一种建立于dCas9工程化修饰蛋白及生物膜层干涉技术基础上的检测核酸的方法与流程
本发明属于生物工程技术领域,涉及一种建立于dcas9工程化修饰蛋白及生物膜层干涉技术基础上的检测核酸的方法,特别是涉及一种基于biotin-dcas9-halo功能化蛋白的crispr-bli检测芯片及其应用。
背景技术:
对病理学相关靶序列标志物的明确促进了核酸检测方法和分子诊断的发展。核酸检测在疾病、食品安全、环境监测等领域有着广泛的应用。其中一些方法在临床环境中发挥着关键作用,提供指导治疗的精确信息,监测患者状况、改善预后。目前广泛应用于靶序列检测的方法有聚合酶链反应(pcr)、基因测序和原位杂交。然而,这些类核酸检测方法大多数较为耗时,需要繁琐的样品处理和试剂配置、探针标记或昂贵仪器支持。因此,发展更适用于临床分子诊断的快速、简便的策略十分迫切。
生物层干涉技术(biolayerinterferometry,bli)是一种实时、灵敏、快速的分析技术,通过监测bli传感器上光学层厚度的变化来检测生物分子间的相互作用。bli目前已经广泛地应用于抗原抗体、药物筛选等重要的医疗卫生领域,在分析生物分子间的相互作用、结合率、解离率和结合特异性等方面具有优势,被许多研究证实为一种快速、敏感、便捷的检测手段。因此,bli技术作为一种靶向核酸检测方法具有很大的潜力。
crispr/cas是一系列在单链rna(sgrna)引导下特异性识别靶序列的核酸酶,核酸。这种基因“魔剪”已经扩展到几乎所有的基因组目标,并被视为一种新型的核酸感受器受到越来越多的关注。dcas9作为crispr/cas9的突变体,其ruvc1和hnh结构域中的两个核酸酶活性位点同时发生突变,使其失去核酸酶活力但仍可对核酸特异性识别,因此dcas9可避免了cas9酶切功能对待检测基因进行剪切等不良作用而作为核酸感受器应用于核酸实现核酸检测中。专利cn107574226a通过利用ru(bpy)32+修饰的dcas9和磁性微球构建一种核酸检测技术。但在核酸的实际检测过程中,ru(bpy)32+强正电性都会导致核酸的非特异性结合捕获,同时检测过程需要多步骤的处理,这使得检测体系复杂耗时,检测特异性减弱。
但目前还很少见有将dcas9与bli技术联合检测核酸的报道。
技术实现要素:
针对上述现有技术,本发明的目的是提供一种基于biotin-dcas9-halo功能化蛋白的crispr-bli检测芯片及其应用。本发明通过halo标签生物特性对dcas9-halo蛋白进行生物素标记,得到一种biotin-dcas9-halo工程化的修饰蛋白;在此基础上,制备crispr探针,并将其固定化到bli传感器表面获得crispr-bli检测芯片;利用crispr-bli检测芯片对核酸的光学信号响应构建一种实时、快速、特异、高通量的核酸检测方法,在无需扩增的条件下就可对核酸进行检测,方法灵敏度高、特异性好。
为实现上述目的,本发明采用如下技术方案:
本发明的第一方面,提供一种crispr-bli检测芯片,包括:bli感受器和固定在bli感受器上的crispr探针;
所述crispr探针由biotin-dcas9-halo功能化蛋白和sgrna复合而成;所述biotin-dcas9-halo功能化蛋白为dcas9-halo蛋白经生物素定点修饰获得,dcas9-halo蛋白的氨基酸序列如seqidno.4所示。
优选的,所述sgrna的序列如seqidno.6所示。
本发明的第二方面,提供上述crispr-bli检测芯片的制备方法,包括以下步骤:
(1)将编码dcas9和halo标签的基因序列连接到表达载体上,获得重组表达质粒,并转化到大肠杆菌中进行原核表达,分离纯化得到dcas9-halo蛋白;将dcas9-halo蛋白进行生物素定点修饰,制备得到biotin-dcas9-halo功能化蛋白;
(2)将biotin-dcas9-halo功能化蛋白与sgrna复合,制备得到crispr探针;
(3)将crispr探针固定在bli感受器上,制备得到crispr-bli检测芯片。
优选的,步骤(1)中,编码dcas9的基因序列如seqidno.1所示;编码halo标签的基因序列如seqidno.2所示。
优选的,步骤(1)中,对dcas9-halo蛋白进行生物素定点修饰的方法为:用ph=7.4的pbs缓冲液将dcas9-halo蛋白超滤浓缩,使蛋白的终浓度大于或等于1mg/ml;向浓缩后的dcas9-halo蛋白溶液中加入halotag@pge-biotinligand母液,混匀,室温反应30-90分钟,以ph=7.4的pbs缓冲液为流动相过除盐柱,除去未反应小分子,收集浓缩修饰后蛋白。
优选的,步骤(2)中,biotin-dcas9-halo功能化蛋白与sgrna复合的方法为:将500μgbiotin-dcas9-halo功能化蛋白超滤浓缩至500~1000μl;取100-250μl的sgrna加入到浓缩后的biotin-dcas9-halo溶液中,混合均匀,在37℃条件下孵育复合15-30分钟。
优选的,步骤(3)中,将crispr探针固定在bli感受器上的方法为:将bli感受器首先浸入平衡液1中平衡基线60-120秒,然后浸入crispr探针溶液中500-900秒,将crispr探针固定在bli感受器上;
所述平衡液1为:含有5-50μg/ml肝素钠、0.1~0.01%bsa、0.01~0.05%tritonx-100、0.01~0.05%tween-20、0.1~0.5mol/lnacl、1~5mmol/lmgcl2、1~5mmol/mledta和0.1~0.01%变性鲑鱼精dna的0.1mpbs,ph=6.0-8.0。
本发明的第三方面,提供上述crispr-bli检测芯片在如下(1)或(2)中的应用:
(1)检测核酸;
(2)制备检测核酸的产品。
本发明的第四方面,提供一种利用上述crispr-bli检测芯片检测核酸的方法,包括以下步骤:
(1)将上述crispr-bli检测芯片浸入1xpbs缓冲液中60-120秒,平衡bli信号基线;
(2)将步骤(1)平衡bli信号基线后的crispr-bli检测芯片浸入到系列浓度的dna标准品中200-500秒,结合信号由bli进行实时输出;
(3)将步骤(2)处理后的crispr-bli检测芯片浸入1xpbs缓冲液中200-500秒,使dna标准品从crispr-bli检测芯片上解离下来;
(4)构建bli响应信号与dna标准品浓度之间的标准曲线,根据标准曲线对待测样品中的核酸进行检测。
优选的,dna标准品的序列如seqidno.5所示。
本发明的有益效果:
(1)本发明调取化脓链球菌(streptococcuspyogene)的crispr/cas9基因,利用基因重组和分子生物学方法得到具有halo标签的核酸酶失活dcas9重组蛋白:dcas9-halo;此重组蛋白可在halo标签的生物特性下简单、快速、稳定的修饰,得到biotin-dcas9-halo工程化蛋白;相较其他修饰手法,本发明能最大程度的保留着dcas9与核酸的特异性亲和力。
(2)本发明将biotin-dcas9-halo功能化蛋白与生物膜层干涉技术(bli)相结合,制备crispr-bli检测芯片;在此基础上,本发明构建了一种新型的核酸检测方法;其中,crispr-bli检测芯片上固定的crispr探针将目标dna特异性捕获至芯片表面,使其光学性质发生改变,通过检测芯片光学信号响应实现对核酸的检测;crispr探针有效提高检测体系的特异性,检测芯片具有实时、快速、灵敏、特异的特点,为高通量输出快速准确的核酸检测结果提供有效手段。
(3)为配合crispr-bli芯片的核酸检测,本发明在检测体系中还开发了检测试剂,能有效减少crispr探针与核酸的非特异结合。
附图说明
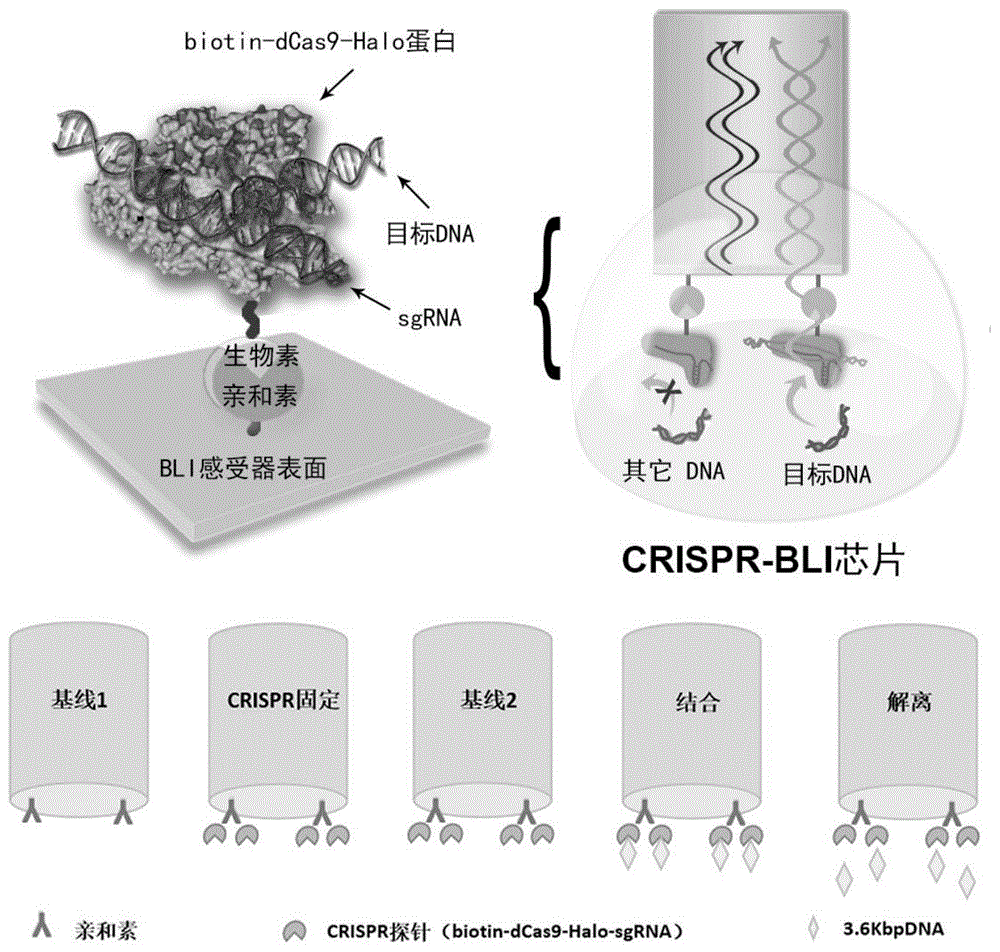
图1:本发明的检测原理示意图;biotin-dcas9-halo与sgrna复合形成crispr探针,通过生物素-亲和素作用固定到bli感受器表面制备得到crispr-bli核酸检测芯片。crispr探针将目标dna特异性捕获至芯片表面,使其光学性质发生改变,通过检测芯片光学信号响应实现对核酸的检测。响应值(bli膜层光学厚度)与靶dna浓度成正比,以此实现对核酸的检测。整个过程分为:平衡(基线1)、crispr固定、再平衡(基线2)、结合、解离;通过前两步制备crispr-bli检测芯片,通过后三步进行核酸检测。
图2:本发明制备的dcas9-halo和biotin-dcas9-halo的sds-page蛋白电泳图;其中,1道为dcas9-halo样本,2道是marker,3道是biotin-dcas9-halo样本。
图3:本发明所述biotin-dcas9-halo在sgrna指导下与非特异dna(左图;1-3道)以及目标dna(右图;4-6道)结合的凝胶阻滞实验;其中,1和4道是marker,2道为biotin-dcas9-halo+sgrna+dna1,3道为biotin-dcas9-halo+dna1,5道为biotin-dcas9-halo+sgrna+目标dna,6道为biotin-dcas9-halo+目标dna;其中,dna1为非特异dna。
图4:本发明所述biotin-dcas9-halo与亲和素修饰微球(mbs-sa)结合后的热释放实验;其中,1道是marker,2道为dcas9-halo+mbs-sa,3道为biotin-dcas9-halo(biotin:dcas9-halo=20:1,摩尔比)+mbs-sa,4道为biotin-dcas9-halo(biotin:dcas9-halo=2:1,摩尔比)+mbs-sa。
图5:crispr-bli检测芯片在检测过程中(结合和解离步骤;图1所示)的实时信号。信号从上到下依次对应标准品s6、s5、s4、s3、s2、s1。
图6:应用crispr-bli检测芯片对核酸进行检测的新型方法学的工作曲线。
图7:通过氨基-羧基反应修饰形成的biotin-dcas9(上排,hyd-b/dcas9表示生物素分子与dcas9蛋白的摩尔比)与通过halo标签与其halotag@pge-biotinligand配体进行修饰的biotin-halo-dcas9(下排,ligand-b/dcas9表示生物素分子与dcas9蛋白的摩尔比)在sgrna指导下与目标dna结合的凝胶阻滞电泳结果;条带的靠上滞后(虚线位置为滞后)表明dcas9与dna的结合。
图8:不同含量目标dna在pcr后经crispr-bli检测的实时信号(a)和拟合曲线(b)。
图9:crispr-bli特异性验证;(a)alp-pcr产物与puc19-pcr产物(阴性对照)的bli信号;(b)40nmalp目标dna与40nmpuc19(阴性对照)的bli信号;(c)两个特异性对照实验的信号对比柱状图,针对两种体系,其非特异性分别为25.1%(a)和13.9%(b)。
具体实施方式
应该指出,以下详细说明都是例示性的,旨在对本申请提供进一步的说明。除非另有指明,本文使用的所有技术和科学术语具有与本申请所属技术领域的普通技术人员通常理解的相同含义。
术语说明:
室温:本文中的“室温”,表示的温度范围为15-30℃。
正如背景技术部分所介绍的,生物膜层干涉技术(bli)作为一种靶向核酸检测方法具有很大的潜力,但目前还很少见有将dcas9与bli技术联合检测核酸的报道。
一般利用bli平台进行核酸分析多是通过先将目标dna进行标记(含标记的引物扩增、裸露磷酸根修饰标记)修饰到bli表面,再与蛋白结合方式进行检测。本发明将dcas9-sgrna复合物(drnp)修饰在bli表面,通过drnp识别dna的方式进行检测,因此dna不需要标记处理,可直接上样。同时,与其他如凝血酶(识别特定序列的dna配体)、dna抗体(识别所有dna序列)相比,drnp可通过对sgrna序列的设计对绝大多数序列进行特异识别,能够对各种序列目标dna进行检测,并保证信号的特异性。
dcas9是cas9核酸酶的突变体(hnh结构域中h840a,ruvc结构域中d10a),dcas9可在sgrna的指导下精确靶向结合dna但不会水解dna骨架,其野生型来自化脓链球菌(streptococcuspyogene),命名为spcas9,详见参考文献:genomeengineeringusingcrispr-cas9system,congl,zhangf,methodsinmolecularbiology(clifton,n.j.)1239(2015):197。halo标签是由微生物紫红红球菌(rhodococcusrhodochrous)的脱卤素酶(dehalogenase)演化而来。该酶可把卤代烷烃(haloalkanes)中的卤素取代基去除,通过置换脱卤素酶活性中心的组氨酸,使得去卤素反应的第二步反应速度大大降低,从而令烷基残基可以有效地以共价键形式结合于蛋白上。详见参考文献:halotagtminterchangeablelabelingtechnologyforcellimagingandproteincapture.los,g.v.etal.,cellnotes11(2005):2-6。
本发明所涉及的dcas9-halo重组蛋白,是经由dcas9和halo标签基因重组而来。将编码dcas9(密码子优化后的基因序列如seqidno.1所示,经密码子优化后,其能更好的在原核表达系统中表达)和halo标签(序列如seqidno.2所示)的基因序列优化后连接到表达载体pet16b上获得重组表达质粒,并转化到大肠杆菌e.colibl21(de3)中得到表达dcas9-halo的工程菌。工程菌进行表达所得产物为可溶性蛋白,通过超声破碎、镍离子亲和柱、疏水层析和离子交换层析进行分离纯化得到纯净的目标,即dcas9-halo蛋白,其氨基酸序列如seqidno.4所示。
本发明所述的biotin-dcas9-halo功能化蛋白为dcas9-halo蛋白经由生物素定点修饰获得,其方法如下:
1.将1mldcas9-halo(1-2mg)用ph=7.4的pbs缓冲液稀释至5ml,用50kda分子量超滤筒超滤浓缩至1ml;
2.重复上述超滤浓缩步骤2次,目的为更换缓冲液,提高修饰效率;
3.取5-20μlhalotag@pge-biotinligand母液(购于promega,g8592)加入到dcas9-halo蛋白溶液中,均匀混合,室温反应30-90分钟;
4.用ph=7.4的pbs缓冲液为流动相过g25除盐柱除去未反应小分子;
5.收集含biotin-dcas9-halo蛋白的洗脱液,超滤浓缩,得到biotin-dcas9-halo功能化蛋白。
本发明采用halotag@pge-biotinligand(halo配体)对dcas9-halo蛋白进行定点修饰,halotag@pge-biotinligand只与halo标签反应连接在halo标签的催化口袋中。在halo的催化下,halo配体与halo标签形成不可逆的共价键而被特异性的修饰到功能蛋白上。这使得halo-dcas9蛋白不会因halo配体的修饰而损失与dna的识别结合能力。与之相比,通过氨基-羧基反应标记的手段可能将生物素连接到dcas9与sgrna/dna结合口袋上(口袋中氨基羧基丰富)降低dcas9与dna的识别结合能力(图7);因此,通过halo-配体的方法更好的保持了原有dcas9的结合能力,不会像nhs-biotin这类会非特异性的与蛋白上的氨基基团反应。
基于biotin-dcas9-halo功能化蛋白,本发明进一步构建了一种对核酸进行特异识别的crispr-bli检测芯片,其结构如图1所示,crispr-bli检测芯片通过将crispr探针固定在bli感受器上制备获得,其方法如下:
1.biotin-dcas9-halo功能化蛋白与指导sgrna进行复合制备crispr探针:
用ph=7.4的pbs缓冲液将biotin-dcas9-halo功能化蛋白浓缩至0.5~1mg/ml,按照sgrna:biotin-dcas9-halo为2:1~5:1(摩尔比)的比例加入sgrna,混合均匀,在37℃条件下孵育复合15-30分钟,得到由biotin-dcas9-halo与sgrna形成的复合物,即crispr探针;具体如下:
(1)用50kda分子量超滤筒将500μgbiotin-dcas9-halo功能化蛋白超滤浓缩至500~1000μl;
(2)取100-250μlsgrna加入到上步所述的biotin-dcas9-halo溶液中,混合均匀,在37℃条件下孵育复合15-30分钟;
(3)用ph=7.4的pbs缓冲液稀释上步所述溶液至2.5ml,用50kda分子量超滤筒将溶液超滤浓缩至500μl;
(4)重复上述步骤5次,得到由biotin-dcas9-halo与sgrna形成的复合物溶液,即crispr探针溶液。
2.通过将crispr探针固定在bli传感器上制备crispr-bli检测芯片:
(1)将平衡液1加入到bli分析用96孔板中,200μl/孔;
(2)将crispr探针溶液(用1xpbs缓冲液将crispr探针稀释至10-50μg/ml)加入到bli分析用96孔板中,200μl/孔;
(3)将平衡液2加入到bli分析用96孔板中,200μl/孔;
(4)将96孔板置于bli分析仪中,执行“loading”步骤,bli仪器会将拾取的感受器首先浸入平衡液1平衡基线60-120秒,然后浸入crispr探针溶液中固定探针500-900秒,得到crispr-bli检测芯片。
本发明开发设计了一种建立在crispr探针及生物膜层干涉技术(bli)基础上的检测核酸手段,其检测原理如图1所示。检测试剂包含平衡液1、crispr探针溶液、平衡液2、样本溶液、解离液五项,分列加入到bli测试用96孔板中,bli仪器拾取感受器后依次经由上述五种溶液进行平衡、探针固定、再平衡、结合和解离步骤,实现crispr-bli检测芯片的制备与核酸的检测。
在发明所述的检测过程中,crispr探针通过生物素-亲和素相互作用固定到bli感受器上,得到crispr-bli检测芯片。当将芯片浸入样本后,样本中含有靶核酸会被芯片上固定的crispr探针特异性的识别结合到crispr-bli检测芯片表面,这将导致芯片表面光学性质发生改变,从而通过检测crispr-bli检测芯片的bli信号响应来测定靶核酸,待测dna片段与bli响应值成正相关。
本发明所述的由crispr-bli检测芯片特异性检测核酸的操作方法如下:
1.将制备好的crispr-bli芯片浸入平衡液2中60-120秒,平衡bli信号基线(baseline);
2.将上步骤所述的crispr-bli芯片浸入到样品液中200-500秒,结合信号由bli进行实时输出(associationanddetection);
3.将上步骤所述的crispr-bli芯片浸入解离液中200-500秒,使测试样本从crispr-bli芯片上解离下来(dissociation);
4.将bli实时响应信号通过软件拟合处理并输出,实现对dna样本的检测。
平衡液1、平衡液2和解离液成分均为1xpbs,优化后1xpbs的组成为:含有5-50μg/ml肝素钠、0.1~0.01%bsa、0.01~0.05%tritonx-100、0.01~0.05%tween-20、0.1~0.5mol/lnacl、1~5mmol/lmgcl2、1~5mmol/mledta、0.1~0.01%变性鲑鱼精dna的0.1mpbs,ph6.8~8.0。肝素能够竞争消除核酸与crispr探针的非特异结合,bsa、tritonx-100、tween-20、变性鲑鱼精dna起到封闭与降低非特异性蛋白、核酸吸附的作用,nacl、mgcl2、edta在溶液中稳定crispr探针,更好的发挥识别结合功能。
优化的,crispr探针溶液为用1xpbs稀释的crispr探针溶液;样本液为2xpbs溶液与核酸样品1:1混合后的待测溶液。
综上,本发明引入biotin-dcas9-halo功能化蛋白,其结合sgrna后形成crispr探针,通过crispr探针对待测核酸片段进行识别捕获,从而将目标核酸特异性的捕获到固定有探针的crispr-bli芯片表面,引起bli信号的改变,以此对核酸进行检测。与之相比,本发明具有如下技术优点:1.通过halo标签与halotag@pge-biotinligand的定点识别与连接修饰dcas9-halo蛋白,相较小分子与蛋白非特异共价反应有更高的连接效率,蛋白功能丧失更小;2.由于通过crispr探针对待测核酸进行直接捕获,免去对待测核酸进行生物素标记的处理,检测更便捷;3.体系不含带强正电的ru(bpy)32+这类分子,同时对试剂成分进行优化,大大较低与电负性较强的核酸之间的非特异相互作用;4.本发明基于bli检测平台具有实时、快速、灵敏、免标记的特点。
为了使得本领域技术人员能够更加清楚地了解本申请的技术方案,以下将结合具体的实施例详细说明本申请的技术方案。如果实施例中未注明的实验具体条件,通常按照常规条件,或者按照试剂公司所推荐的条件;下述实施例中所用的试剂、耗材等,如无特殊说明,均可通过商业途径获得。
实施例1:(e.coli)功能化biotin-dcas9-halo蛋白的制备
(1)dcas9-halo表达载体的构建
dcas9基因片段通过基因合成、密码子优化及pcr得到,在5’端引入xbai酶切位点(tctaga),3’端引入ccaccgaggtctaga序列;halo基因片段从商品化质粒中经pcr得到,在5’端引入ggtggctccagatct序列,3’端引入xhoi酶切位点(ctcgag)经pcr和xbai和xhoi双酶切,将dcas9-halo重组基因(序列如seqidno.3所示)克隆到pet16b的质粒上,获得重组载体pet16b-dcas9-halo,测序验证。
酶切体系如下(20μl):
连接体系如下(20μl):
(2)dcas9-halo的表达、纯化
将pet16b-dcas9-halo表达载体转化进入e.coilbl21(ed3)感受态细胞中,操作如下:将-80℃冰箱保存的感受态细胞置于冰中融化5min。加入表达载体pet16b-dcas9-halo2μl,轻轻混匀后冰上放置30min。42℃水浴锅中放置90s后,立即于冰中放置2min。每管加入800μl预温的lb培养基,37℃培养45min(160r/min)。4000rpm离心1min后,取沉淀涂布平板,将平板倒置于37℃恒温培养箱中培养过夜,培养形成单一菌落。
挑取上步所得单一菌落至含有100μg/ml氨苄的lb培养基中(20ml),37℃、180r/min振荡培养过夜,获得种子液。将种子液以1%(v/v)的比例接种量接种至2l含有100μg/ml氨苄的lb培养基中,37℃、180r/min振荡培养至od600=0.6-0.8,然后加入iptg至终浓度为0.2mmol/l,18℃、180r/min继续振荡培养18h,离心收集菌体-80摄氏度冻存。
菌体中纯化dcas9-halo方法如下:配置缓冲液a(ph7.5tris-hcl)的配方:取24.2gtris-base置于1l烧杯中,加入约800ml去离子水充分搅拌溶解,用浓hcl调ph至7.5,将溶液用容量瓶定容至1l,4℃保存。使用时稀释10倍。缓冲液b(ph8.0tris-hcl)的配方:取24.2gtris-base置于1l烧杯中,加入约800ml去离子水充分搅拌溶解,用浓hcl调ph至8.0,将溶液用容量瓶定容至1l,4℃保存。使用时稀释10倍。
取冻存工程菌重悬于缓冲液a中,浓度为1g/ml,置于冰上超声破碎20min(分2次),当菌液由粘稠状态变为透亮即可,4℃、12000r/min离心30min,收集上清蛋白液,对上清液中可溶的dcas9进行ni柱亲和纯化,所得洗脱液加入氯化钠至终浓度1m,经phenylhp疏水层析纯化,用含有氯化钠浓度为1.5m-0m的缓冲液a线性洗脱,page电泳验证,收集并合并目的蛋白,将收集的蛋白液用缓冲液b透析过夜除盐;将透析后的蛋白液进行highs阳离子交换层析,用含nacl浓度为0m-0.5m的缓冲液b线性洗脱,page电泳验证,收集并合并目的蛋白,将收集的蛋白液用缓冲液b透析过夜除盐;将透析后的蛋白液再次进行highs阳离子交换层析,用含nacl浓度为0.1m-1m的缓冲液b线性洗脱,收集并合并目的蛋白,用缓冲液b透析除盐后,即得到本发明所述的dcas9-halo蛋白,其sds-page电泳结果如图2道1所示,其氨基酸序列如seqidno.4所示。
(3)biotin-dcas9-halo的制备
将1mldcas9-halo(1-2mg)用ph=7.4的pbs缓冲液稀释至5ml,用50kda分子量超滤筒超滤浓缩至1ml;重复超滤浓缩步骤2次,目的为更换缓冲液,提高修饰效率;取5-20μlhalotag@pge-biotinligand母液加入到dcas9-halo蛋白溶液中,均匀混合,室温反应30-90分钟。用ph=7.4的pbs缓冲液为流动相过g25除盐柱除去未反应小分子。收集含biotin-dcas9-halo蛋白的洗脱液,超滤浓缩,得到biotin-dcas9-halo,其sds-page电泳结果如图2中泳道3所示。
实施例2:biotin-dcas9-halo功能蛋白的特征
(1)biotin-dcas9-halo功能蛋白的特异性识别
功能化biotin-dcas9-halo可在sgrna指导下与序列特异性双链dna片段结合。本发明通过设计合成指导sgrna(序列如seqidno.6所示),验证biotin-dcas9-halo与dna(dna序列如seqidno.5所示)特异性结合,我们用凝胶阻滞电泳验证了功能蛋白的特异性识别,当biotin-dcas9-halo-sgrna与dna1特异性结合形成复合物,非变性电泳下其迁移率要小于游离的dna1,表现为复合物中dna条带比未形成复合物的dna条带靠上。
凝胶阻滞电泳方法如下
1)5%非变性page胶的配置
2)电泳条件:0.5xtbe缓冲液作为电泳液,4℃,120v,1h。
凝胶阻滞电泳结果如图3所示。
(2)biotin-dcas9-halo功能蛋白的固定
功能化biotin-dcas9-halo可在生物素-亲和素相互作用下固定在bli感受器表面。本发明通过亲和素修饰的磁性微球结合拾取biotin-dcas9-halo功能蛋白,通过磁性微球拾取效率验证biotin-dcas9-halo功能蛋白的固定能力,并与未修饰的dcas9-halo进行对比。实验中,被磁球吸附的biotin-dcas9-halo可经过多次洗涤,加热的方式从磁球固定相中释放下来,释放的蛋白量可表征功能蛋白的固定能力。热释放实验手法如下:
取5-10μg的biotin-dcas9-halo蛋白加入由pbs缓冲液(20mmpbs,0.15mnacl,0.05bsa,0.1%v/v甘油,20mmedta;ph7.0)悬浮的亲和素修饰的磁性微球(500μg)中,混匀,37℃孵育30分钟。用pbs缓冲液洗涤五次后,磁性微球重悬于20μl的1xsdspage上样缓冲液中,95℃加热5分钟,12000rpm/分离心5分钟去除磁性微球,上清液通过sds-page进行分析;电泳条件:110v,1h;热释放结果如图4所示。结果表明:当生物素配体分子与dcas9-halo蛋白摩尔比大于2进行修饰时,所得到的biotin-dcas9-halo功能蛋白就能有效的固定。
实施例3:应用crispr-bli检测芯片进行核酸定量检测
1)配置2xpbs缓冲液:0.2mpbs(ph6.8~8.0),其中含肝素钠(10-100μg/ml)、bsa(0.2~0.02%)、tritonx-100(0.02~0.1%)、tween-20(0.02~0.1%)、nacl(0.2~1.0mol/l)、mgcl2(2~10mmol/l)、edta(2~10mmol/ml)、变性鲑鱼精dna(0.2~0.02%);同时稀释2倍配置成1xpbs。
2)配置crispr探针溶液:biotin-dcas9-halo蛋白与sgrna复合后的crispr探针用1xpbs稀释,终浓度为10-50μg/ml。
3)配置dna标准品:dna标准品(s1-s6)由dna溶液与2xpbs以体积比1:1混合形成,各标准品浓度依次为:s1:2.5nm,s2:5nm,s3:10nm,s4:20nm,s5:40nm,s6:80nm。其中dna标准品的核苷酸序列如seqidno.5所示,长度为3.6kbp。
4)用排枪向bli的96孔样品板中依次加入1xpbs,crispr探针溶液,1xpbs,dna标准品,1xpbs分别作为平衡液1,crispr探针液,平衡液2,样品液,解离液;然后将96孔样品板放入bli仪器中。
5)设置仪器参数,测试模式:动力学;测试参数:平衡(baseline1)60-120秒,固定(loading)500-900秒,再平衡(baseline2)100-200秒,结合(association)200-500秒,解离(dissociation)200-500秒,温度20-40℃。
点击开始,由octetred96e软件实时报告各crispr-bli检测芯片的信号值,进行分析拟合,实时信号如图5所示;方法学标准曲线如图6所示。针对3.6kbp的dna,本发明的灵敏度为840pmol/l(3.8ng/μl)。
实施例4:方法学考察
1.灵敏度:
bli信号与结合到其表面分析物大小有关,未借助扩增等手段时,针对3.6kbp的灵敏度为840pmol/l(3.8ng/ul),但当dna样本大小从3.6kbp改变至基因组水平(1.9×1012gmol-1;~2.9gb),灵敏度能达到1.9fm。
当在检测前对目标dna进行15个循环的pcr扩增后,体系检测限(lod)可降低到20pg(按pcr加入的目标dna模板量计)。结果见图8。
2.特异性
针对crispr-bli特异性,利用碱性磷酸酶基因(alp)目标序列为样本,以等质量的puc19为阴性对照测定响应信号,检测体系特异性。相似的,以alp目标序列为模板进行pcr,并以等质量的puc19模板所获得的pcr产物为阴性对照测定响应信号,检测体系特异性。结果见图9。
以上所述仅为本申请的优选实施例而已,并不用于限制本申请,对于本领域的技术人员来说,本申请可以有各种更改和变化。凡在本申请的精神和原则之内,所作的任何修改、等同替换、改进等,均应包含在本申请的保护范围之内。
sequencelisting
<110>济南国科医工科技发展有限公司
<120>基于biotin-dcas9-halo功能化蛋白的crispr-bli检测芯片及其应用
<130>2021
<160>6
<170>patentinversion3.5
<210>1
<211>4104
<212>dna
<213>dcas9序列
<400>1
atggataagaaatactcaataggcttagctatcggcacaaatagcgtcggatgggcggtg60
atcactgatgaatataaggttccgtctaaaaagttcaaggttctgggaaatacagaccgc120
cacagtatcaaaaaaaatcttataggggctcttttatttgacagtggagagacagcggaa180
gcgactcgtctcaaacggacagctcgtagaaggtatacacgtcggaagaatcgtatttgt240
tatctacaggagattttttcaaatgagatggcgaaagtagatgatagtttctttcatcga300
cttgaagagtcttttttggtggaagaagacaagaagcatgaacgtcatcctatttttgga360
aatatagtagatgaagttgcttatcatgagaaatatccaactatctatcatctgcgaaaa420
aaattggtagattctactgataaagcggatttgcgcttaatctatttggccttagcgcat480
atgattaagtttcgtggtcattttttgattgagggagatttaaatcctgataatagtgat540
gtggacaaactatttatccagttggtacaaacctacaatcaattatttgaagaaaaccct600
attaacgcaagtggagtagatgctaaagcgattctttctgcacgattgagtaaatcaaga660
cgattagaaaatctcattgctcagctccccggtgagaagaaaaatggcttatttgggaat720
ctcattgctttgtcattgggtttgacccctaattttaaatcaaattttgatttggcagaa780
gatgctaaattacagctttcaaaagatacttacgatgatgatttagataatttattggcg840
caaattggagatcaatatgctgatttgtttttggcagctaagaatttatcagatgctatt900
ttactttcagatatcctaagagtaaatactgaaataactaaggctcccctatcagcttca960
atgattaaacgctacgatgaacatcatcaagacttgactcttttaaaagctttagttcga1020
caacaacttccagaaaagtataaagaaatcttttttgatcaatcaaaaaacggatatgca1080
ggttatattgatgggggagctagccaagaagaattttataaatttatcaaaccaatttta1140
gaaaaaatggatggtactgaggaattattggtgaaactaaatcgtgaagatttgctgcgc1200
aagcaacggacctttgacaacggctctattccccatcaaattcacttgggtgagctgcat1260
gctattttgagaagacaagaagacttttatccatttttaaaagacaatcgtgagaagatt1320
gaaaaaatcttgacttttcgaattccttattatgttggtccattggcgcgtggcaatagt1380
cgttttgcatggatgactcggaagtctgaagaaacaattaccccatggaattttgaagaa1440
gttgtcgataaaggtgcttcagctcaatcatttattgaacgcatgacaaactttgataaa1500
aatcttccaaatgaaaaagtactaccaaaacatagtttgctttatgagtattttacggtt1560
tataacgaattgacaaaggtcaaatatgttactgaaggaatgcgaaaaccagcatttctt1620
tcaggtgaacagaagaaagccattgttgatttactcttcaaaacaaatcgaaaagtaacc1680
gttaagcaattaaaagaagattatttcaaaaaaatagaatgttttgatagtgttgaaatt1740
tcaggagttgaagatagatttaatgcttcattaggtacctaccatgatttgctaaaaatt1800
attaaagataaagattttttggataatgaagaaaatgaagatatcttagaggatattgtt1860
ttaacattgaccttatttgaagatagggagatgattgaggaaagacttaaaacatatgct1920
cacctctttgatgataaggtgatgaaacagcttaaacgtcgccgttatactggttgggga1980
cgtttgtctcgaaaattgattaatggtattagggataagcaatctggcaaaacaatatta2040
gattttttgaaatcagatggttttgccaatcgcaattttatgcagctgatccatgatgat2100
agtttgacatttaaagaagacattcaaaaagcacaagtgtctggacaaggcgatagttta2160
catgaacatattgcaaatttagctggtagccctgctattaaaaaaggtattttacagact2220
gtaaaagttgttgatgaattggtcaaagtaatggggcggcataagccagaaaatatcgtt2280
attgaaatggcacgtgaaaatcagacaactcaaaagggccagaaaaattcgcgagagcgt2340
atgaaacgaatcgaagaaggtatcaaagaattaggaagtcagattcttaaagagcatcct2400
gttgaaaatactcaattgcaaaatgaaaagctctatctctattatctccaaaatggaaga2460
gacatgtatgtggaccaagaattagatattaatcgtttaagtgattatgatgtcgatgcc2520
attgttccacaaagtttccttaaagacgattcaatagacaataaggtcttaacgcgttct2580
gataaaaatcgtggtaaatcggataacgttccaagtgaagaagtagtcaaaaagatgaaa2640
aactattggagacaacttctaaacgccaagttaatcactcaacgtaagtttgataattta2700
acgaaagctgaacgtggaggtttgagtgaacttgataaagctggttttatcaaacgccaa2760
ttggttgaaactcgccaaatcactaagcatgtggcacaaattttggatagtcgcatgaat2820
actaaatacgatgaaaatgataaacttattcgagaggttaaagtgattaccttaaaatct2880
aaattagtttctgacttccgaaaagatttccaattctataaagtacgtgagattaacaat2940
taccatcatgcccatgatgcgtatctaaatgccgtcgttggaactgctttgattaagaaa3000
tatccaaaacttgaatcggagtttgtctatggtgattataaagtttatgatgttcgtaaa3060
atgattgctaagtctgagcaagaaataggcaaagcaaccgcaaaatatttcttttactct3120
aatatcatgaacttcttcaaaacagaaattacacttgcaaatggagagattcgcaaacgc3180
cctctaatcgaaactaatggggaaactggagaaattgtctgggataaagggcgagatttt3240
gccacagtgcgcaaagtattgtccatgccccaagtcaatattgtcaagaaaacagaagta3300
cagacaggcggattctccaaggagtcaattttaccaaaaagaaattcggacaagcttatt3360
gctcgtaaaaaagactgggatccaaaaaaatatggtggttttgatagtccaacggtagct3420
tattcagtcctagtggttgctaaggtggaaaaagggaaatcgaagaagttaaaatccgtt3480
aaagagttactagggatcacaattatggaaagaagttcctttgaaaaaaatccgattgac3540
tttttagaagctaaaggatataaggaagttaaaaaagacttaatcattaaactacctaaa3600
tatagtctttttgagttagaaaacggtcgtaaacggatgctggctagtgccggagaatta3660
caaaaaggaaatgagctggctctgccaagcaaatatgtgaattttttatatttagctagt3720
cattatgaaaagttgaagggtagtccagaagataacgaacaaaaacaattgtttgtggag3780
cagcataagcattatttagatgagattattgagcaaatcagtgaattttctaagcgtgtt3840
attttagcagatgccaatttagataaagttcttagtgcatataacaaacatagagacaaa3900
ccaatacgtgaacaagcagaaaatattattcatttatttacgttgacgaatcttggagct3960
cccgctgcttttaaatattttgatacaacaattgatcgtaaacgatatacgtctacaaaa4020
gaagttttagatgccactcttatccatcaatccatcactggtctttatgaaacacgcatt4080
gatttgagtcagctaggaggtgac4104
<210>2
<211>708
<212>dna
<213>halo标签序列
<400>2
atggcagaaatcggtactggctttccattcgacccccattatgtggaagtcctgggcgag60
cgcatgcactacgtcgatgttggtccgcgcgatggcacccctgtgctgttcctgcacggt120
aacccgacctcctcctacgtgtggcgcaacatcatcccgcatgttgcaccgacccatcgc180
tgcattgctccagacctgatcggtatgggcaaatccgacaaaccagacctgggttatttc240
ttcgacgaccacgtccgcttcatggatgccttcatcgaagccctgggtctggaagaggtc300
gtcctggtcattcacgactggggctccgctctgggtttccactgggccaagcgcaatcca360
gagcgcgtcaaaggtattgcatttatggagttcatccgccctatcccgacctgggacgaa420
tggccagaatttgcccgcgagaccttccaggccttccgcaccaccgacgtcggccgcaag480
ctgatcatcgatcagaacgtttttatcgagggtacgctgccgatgggtgtcgtccgcccg540
ctgactgaagtcgagatggaccattaccgcgagccgttcctgaatcctgttgaccgcgag600
ccactgtggcgcttcccaaacgagctgccaatcgccggtgagccagcgaacatcgtcgcg660
ctggtcgaagaatacatggactggctgcaccagtcccctgtcccgaag708
<210>3
<211>5031
<212>dna
<213>dcas9-halo基因序列
<400>3
atgcatcatcatcatcatcacgtggataagaaatactcaataggcttagctatcggcaca60
aatagcgtcggatgggcggtgatcactgatgaatataaggttccgtctaaaaagttcaag120
gttctgggaaatacagaccgccacagtatcaaaaaaaatcttataggggctcttttattt180
gacagtggagagacagcggaagcgactcgtctcaaacggacagctcgtagaaggtataca240
cgtcggaagaatcgtatttgttatctacaggagattttttcaaatgagatggcgaaagta300
gatgatagtttctttcatcgacttgaagagtcttttttggtggaagaagacaagaagcat360
gaacgtcatcctatttttggaaatatagtagatgaagttgcttatcatgagaaatatcca420
actatctatcatctgcgaaaaaaattggtagattctactgataaagcggatttgcgctta480
atctatttggccttagcgcatatgattaagtttcgtggtcattttttgattgagggagat540
ttaaatcctgataatagtgatgtggacaaactatttatccagttggtacaaacctacaat600
caattatttgaagaaaaccctattaacgcaagtggagtagatgctaaagcgattctttct660
gcacgattgagtaaatcaagacgattagaaaatctcattgctcagctccccggtgagaag720
aaaaatggcttatttgggaatctcattgctttgtcattgggtttgacccctaattttaaa780
tcaaattttgatttggcagaagatgctaaattacagctttcaaaagatacttacgatgat840
gatttagataatttattggcgcaaattggagatcaatatgctgatttgtttttggcagct900
aagaatttatcagatgctattttactttcagatatcctaagagtaaatactgaaataact960
aaggctcccctatcagcttcaatgattaaacgctacgatgaacatcatcaagacttgact1020
cttttaaaagctttagttcgacaacaacttccagaaaagtataaagaaatcttttttgat1080
caatcaaaaaacggatatgcaggttatattgatgggggagctagccaagaagaattttat1140
aaatttatcaaaccaattttagaaaaaatggatggtactgaggaattattggtgaaacta1200
aatcgtgaagatttgctgcgcaagcaacggacctttgacaacggctctattccccatcaa1260
attcacttgggtgagctgcatgctattttgagaagacaagaagacttttatccattttta1320
aaagacaatcgtgagaagattgaaaaaatcttgacttttcgaattccttattatgttggt1380
ccattggcgcgtggcaatagtcgttttgcatggatgactcggaagtctgaagaaacaatt1440
accccatggaattttgaagaagttgtcgataaaggtgcttcagctcaatcatttattgaa1500
cgcatgacaaactttgataaaaatcttccaaatgaaaaagtactaccaaaacatagtttg1560
ctttatgagtattttacggtttataacgaattgacaaaggtcaaatatgttactgaagga1620
atgcgaaaaccagcatttctttcaggtgaacagaagaaagccattgttgatttactcttc1680
aaaacaaatcgaaaagtaaccgttaagcaattaaaagaagattatttcaaaaaaatagaa1740
tgttttgatagtgttgaaatttcaggagttgaagatagatttaatgcttcattaggtacc1800
taccatgatttgctaaaaattattaaagataaagattttttggataatgaagaaaatgaa1860
gatatcttagaggatattgttttaacattgaccttatttgaagatagggagatgattgag1920
gaaagacttaaaacatatgctcacctctttgatgataaggtgatgaaacagcttaaacgt1980
cgccgttatactggttggggacgtttgtctcgaaaattgattaatggtattagggataag2040
caatctggcaaaacaatattagattttttgaaatcagatggttttgccaatcgcaatttt2100
atgcagctgatccatgatgatagtttgacatttaaagaagacattcaaaaagcacaagtg2160
tctggacaaggcgatagtttacatgaacatattgcaaatttagctggtagccctgctatt2220
aaaaaaggtattttacagactgtaaaagttgttgatgaattggtcaaagtaatggggcgg2280
cataagccagaaaatatcgttattgaaatggcacgtgaaaatcagacaactcaaaagggc2340
cagaaaaattcgcgagagcgtatgaaacgaatcgaagaaggtatcaaagaattaggaagt2400
cagattcttaaagagcatcctgttgaaaatactcaattgcaaaatgaaaagctctatctc2460
tattatctccaaaatggaagagacatgtatgtggaccaagaattagatattaatcgttta2520
agtgattatgatgtcgatgccattgttccacaaagtttccttaaagacgattcaatagac2580
aataaggtcttaacgcgttctgataaaaatcgtggtaaatcggataacgttccaagtgaa2640
gaagtagtcaaaaagatgaaaaactattggagacaacttctaaacgccaagttaatcact2700
caacgtaagtttgataatttaacgaaagctgaacgtggaggtttgagtgaacttgataaa2760
gctggttttatcaaacgccaattggttgaaactcgccaaatcactaagcatgtggcacaa2820
attttggatagtcgcatgaatactaaatacgatgaaaatgataaacttattcgagaggtt2880
aaagtgattaccttaaaatctaaattagtttctgacttccgaaaagatttccaattctat2940
aaagtacgtgagattaacaattaccatcatgcccatgatgcgtatctaaatgccgtcgtt3000
ggaactgctttgattaagaaatatccaaaacttgaatcggagtttgtctatggtgattat3060
aaagtttatgatgttcgtaaaatgattgctaagtctgagcaagaaataggcaaagcaacc3120
gcaaaatatttcttttactctaatatcatgaacttcttcaaaacagaaattacacttgca3180
aatggagagattcgcaaacgccctctaatcgaaactaatggggaaactggagaaattgtc3240
tgggataaagggcgagattttgccacagtgcgcaaagtattgtccatgccccaagtcaat3300
attgtcaagaaaacagaagtacagacaggcggattctccaaggagtcaattttaccaaaa3360
agaaattcggacaagcttattgctcgtaaaaaagactgggatccaaaaaaatatggtggt3420
tttgatagtccaacggtagcttattcagtcctagtggttgctaaggtggaaaaagggaaa3480
tcgaagaagttaaaatccgttaaagagttactagggatcacaattatggaaagaagttcc3540
tttgaaaaaaatccgattgactttttagaagctaaaggatataaggaagttaaaaaagac3600
ttaatcattaaactacctaaatatagtctttttgagttagaaaacggtcgtaaacggatg3660
ctggctagtgccggagaattacaaaaaggaaatgagctggctctgccaagcaaatatgtg3720
aattttttatatttagctagtcattatgaaaagttgaagggtagtccagaagataacgaa3780
caaaaacaattgtttgtggagcagcataagcattatttagatgagattattgagcaaatc3840
agtgaattttctaagcgtgttattttagcagatgccaatttagataaagttcttagtgca3900
tataacaaacatagagacaaaccaatacgtgaacaagcagaaaatattattcatttattt3960
acgttgacgaatcttggagctcccgctgcttttaaatattttgatacaacaattgatcgt4020
aaacgatatacgtctacaaaagaagttttagatgccactcttatccatcaatccatcact4080
ggtctttatgaaacacgcattgatttgagtcagctaggaggtgacggtggctccagatct4140
gcagaaatcggtactggctttccattcgacccccattatgtggaagtcctgggcgagcgc4200
atgcactacgtcgatgttggtccgcgcgatggcacccctgtgctgttcctgcacggtaac4260
ccgacctcctcctacgtgtggcgcaacatcatcccgcatgttgcaccgacccatcgctgc4320
attgctccagacctgatcggtatgggcaaatccgacaaaccagacctgggttatttcttc4380
gacgaccacgtccgcttcatggatgccttcatcgaagccctgggtctggaagaggtcgtc4440
ctggtcattcacgactggggctccgctctgggtttccactgggccaagcgcaatccagag4500
cgcgtcaaaggtattgcatttatggagttcatccgccctatcccgacctgggacgaatgg4560
ccagaatttgcccgcgagaccttccaggccttccgcaccaccgacgtcggccgcaagctg4620
atcatcgatcagaacgtttttatcgagggtacgctgccgatgggtgtcgtccgcccgctg4680
actgaagtcgagatggaccattaccgcgagccgttcctgaatcctgttgaccgcgagcca4740
ctgtggcgcttcccaaacgagctgccaatcgccggtgagccagcgaacatcgtcgcgctg4800
gtcgaagaatacatggactggctgcaccagtcccctgtcccgaagctgctgttctggggc4860
accccaggcgttctgatcccaccggccgaagccgctcgcctggccaaaagcctgcctaac4920
tgcaaggctgtggacatcggcccgggtctgaatctgctgcaagaagacaacccggacctg4980
atcggcagcgagatcgcgcgctggctgtctactctggagatttccggttaa5031
<210>4
<211>1676
<212>prt
<213>dcas9-halo蛋白
<400>4
methishishishishishisvalasplyslystyrserileglyleu
151015
alaileglythrasnservalglytrpalavalilethraspglutyr
202530
lysvalproserlyslysphelysvalleuglyasnthrasparghis
354045
serilelyslysasnleuileglyalaleuleupheaspserglyglu
505560
thralaglualathrargleulysargthralaargargargtyrthr
65707580
argarglysasnargilecystyrleuglngluilepheserasnglu
859095
metalalysvalaspaspserphephehisargleuglugluserphe
100105110
leuvalglugluasplyslyshisgluarghisproilepheglyasn
115120125
ilevalaspgluvalalatyrhisglulystyrprothriletyrhis
130135140
leuarglyslysleuvalaspserthrasplysalaaspleuargleu
145150155160
iletyrleualaleualahismetilelyspheargglyhispheleu
165170175
ilegluglyaspleuasnproaspasnseraspvalasplysleuphe
180185190
ileglnleuvalglnthrtyrasnglnleupheglugluasnproile
195200205
asnalaserglyvalaspalalysalaileleuseralaargleuser
210215220
lysserargargleugluasnleuilealaglnleuproglyglulys
225230235240
lysasnglyleupheglyasnleuilealaleuserleuglyleuthr
245250255
proasnphelysserasnpheaspleualagluaspalalysleugln
260265270
leuserlysaspthrtyraspaspaspleuaspasnleuleualagln
275280285
ileglyaspglntyralaaspleupheleualaalalysasnleuser
290295300
aspalaileleuleuseraspileleuargvalasnthrgluilethr
305310315320
lysalaproleuseralasermetilelysargtyraspgluhishis
325330335
glnaspleuthrleuleulysalaleuvalargglnglnleuproglu
340345350
lystyrlysgluilephepheaspglnserlysasnglytyralagly
355360365
tyrileaspglyglyalaserglnglugluphetyrlyspheilelys
370375380
proileleuglulysmetaspglythrglugluleuleuvallysleu
385390395400
asnarggluaspleuleuarglysglnargthrpheaspasnglyser
405410415
ileprohisglnilehisleuglygluleuhisalaileleuargarg
420425430
glngluaspphetyrpropheleulysaspasnargglulysileglu
435440445
lysileleuthrpheargileprotyrtyrvalglyproleualaarg
450455460
glyasnserargphealatrpmetthrarglysserglugluthrile
465470475480
thrprotrpasnpheglugluvalvalasplysglyalaseralagln
485490495
serpheilegluargmetthrasnpheasplysasnleuproasnglu
500505510
lysvalleuprolyshisserleuleutyrglutyrphethrvaltyr
515520525
asngluleuthrlysvallystyrvalthrgluglymetarglyspro
530535540
alapheleuserglygluglnlyslysalailevalaspleuleuphe
545550555560
lysthrasnarglysvalthrvallysglnleulysgluasptyrphe
565570575
lyslysileglucyspheaspservalgluileserglyvalgluasp
580585590
argpheasnalaserleuglythrtyrhisaspleuleulysileile
595600605
lysasplysasppheleuaspasnglugluasngluaspileleuglu
610615620
aspilevalleuthrleuthrleuphegluaspargglumetileglu
625630635640
gluargleulysthrtyralahisleupheaspasplysvalmetlys
645650655
glnleulysargargargtyrthrglytrpglyargleuserarglys
660665670
leuileasnglyileargasplysglnserglylysthrileleuasp
675680685
pheleulysseraspglyphealaasnargasnphemetglnleuile
690695700
hisaspaspserleuthrphelysgluaspileglnlysalaglnval
705710715720
serglyglnglyaspserleuhisgluhisilealaasnleualagly
725730735
serproalailelyslysglyileleuglnthrvallysvalvalasp
740745750
gluleuvallysvalmetglyarghislysprogluasnilevalile
755760765
glumetalaarggluasnglnthrthrglnlysglyglnlysasnser
770775780
arggluargmetlysargileglugluglyilelysgluleuglyser
785790795800
glnileleulysgluhisprovalgluasnthrglnleuglnasnglu
805810815
lysleutyrleutyrtyrleuglnasnglyargaspmettyrvalasp
820825830
glngluleuaspileasnargleuserasptyraspvalaspalaile
835840845
valproglnserpheleulysaspaspserileaspasnlysvalleu
850855860
thrargserasplysasnargglylysseraspasnvalproserglu
865870875880
gluvalvallyslysmetlysasntyrtrpargglnleuleuasnala
885890895
lysleuilethrglnarglyspheaspasnleuthrlysalagluarg
900905910
glyglyleusergluleuasplysalaglypheilelysargglnleu
915920925
valgluthrargglnilethrlyshisvalalaglnileleuaspser
930935940
argmetasnthrlystyraspgluasnasplysleuilearggluval
945950955960
lysvalilethrleulysserlysleuvalseraspphearglysasp
965970975
pheglnphetyrlysvalarggluileasnasntyrhishisalahis
980985990
aspalatyrleuasnalavalvalglythralaleuilelyslystyr
99510001005
prolysleuglusergluphevaltyrglyasptyrlysvaltyr
101010151020
aspvalarglysmetilealalyssergluglngluileglylys
102510301035
alathralalystyrphephetyrserasnilemetasnphephe
104010451050
lysthrgluilethrleualaasnglygluilearglysargpro
105510601065
leuilegluthrasnglygluthrglygluilevaltrpasplys
107010751080
glyargaspphealathrvalarglysvalleusermetprogln
108510901095
valasnilevallyslysthrgluvalglnthrglyglypheser
110011051110
lysgluserileleuprolysargasnserasplysleuileala
111511201125
arglyslysasptrpaspprolyslystyrglyglypheaspser
113011351140
prothrvalalatyrservalleuvalvalalalysvalglulys
114511501155
glylysserlyslysleulysservallysgluleuleuglyile
116011651170
thrilemetgluargserserpheglulysasnproileaspphe
117511801185
leuglualalysglytyrlysgluvallyslysaspleuileile
119011951200
lysleuprolystyrserleuphegluleugluasnglyarglys
120512101215
argmetleualaseralaglygluleuglnlysglyasngluleu
122012251230
alaleuproserlystyrvalasnpheleutyrleualaserhis
123512401245
tyrglulysleulysglyserprogluaspasngluglnlysgln
125012551260
leuphevalgluglnhislyshistyrleuaspgluileileglu
126512701275
glnileserglupheserlysargvalileleualaaspalaasn
128012851290
leuasplysvalleuseralatyrasnlyshisargasplyspro
129513001305
ilearggluglnalagluasnileilehisleuphethrleuthr
131013151320
asnleuglyalaproalaalaphelystyrpheaspthrthrile
132513301335
asparglysargtyrthrserthrlysgluvalleuaspalathr
134013451350
leuilehisglnserilethrglyleutyrgluthrargileasp
135513601365
leuserglnleuglyglyaspglyglyserargseralagluile
137013751380
glythrglyphepropheaspprohistyrvalgluvalleugly
138513901395
gluargmethistyrvalaspvalglyproargaspglythrpro
140014051410
valleupheleuhisglyasnprothrsersertyrvaltrparg
141514201425
asnileileprohisvalalaprothrhisargcysilealapro
143014351440
aspleuileglymetglylysserasplysproaspleuglytyr
144514501455
phepheaspasphisvalargphemetaspalapheilegluala
146014651470
leuglyleuglugluvalvalleuvalilehisasptrpglyser
147514801485
alaleuglyphehistrpalalysargasnprogluargvallys
149014951500
glyilealaphemetglupheileargproileprothrtrpasp
150515101515
glutrpprogluphealaarggluthrpheglnalapheargthr
152015251530
thraspvalglyarglysleuileileaspglnasnvalpheile
153515401545
gluglythrleuprometglyvalvalargproleuthrgluval
155015551560
glumetasphistyrargglupropheleuasnprovalasparg
156515701575
gluproleutrpargpheproasngluleuproilealaglyglu
158015851590
proalaasnilevalalaleuvalgluglutyrmetasptrpleu
159516001605
hisglnserprovalprolysleuleuphetrpglythrprogly
161016151620
valleuileproproalaglualaalaargleualalysserleu
162516301635
proasncyslysalavalaspileglyproglyleuasnleuleu
164016451650
glngluaspasnproaspleuileglysergluilealaargtrp
165516601665
leuserthrleugluilesergly
16701675
<210>5
<211>3627
<212>dna
<213>dna标准品
<400>5
tccgtaagatgcttttctgtgactggtgagtactcaaccaagtcattctgagaatagtgt60
atgcggcgaccgagttgctcttgcccggcgtcaacacgggataataccgcgccacatagc120
agaactttaaaagtgctcatcattggaaaacgttcttcggggcgaaaactctcaaggatc180
ttaccgctgttgagatccagttcgatgtaacccactcgtgcacccaactgatcttcagca240
tcttttactttcaccagcgtttctgggtgagcaaaaacaggaaggcaaaatgccgcaaaa300
aagggaataagggcgacacggaaatgttgaatactcatactcttcctttttcaatattat360
tgaagcatttatcagggttattgtctcatgagcggatacatatttgaatgtatttagaaa420
aataaacaaataggggttccgcgcacatttccccgaaaagtgccacctgacgtctaagaa480
accattattatcatgacattaacctataaaaataggcgtatcacgaggccctttcgtctt540
caagaattctcatgtttgacagcttatcatcgataagctttaatgcggtagtttatcaca600
gttaaattgctaacgcagtcaggcaccgtgtatgaaatctaacaatgcgctcatcgtcat660
cctcggcaccgtcaccctggatgctgtaggcataggcttggttatgccggtactgccggg720
cctcttgcgggatatccggatatagttcctcctttcagcaaaaaacccctcaagacccgt780
ttagaggccccaaggggttatgctagttattgctcagcggtggcagcagccaactcagct840
tcctttcgggctttgttagcagccggatgaaacaaagcactattgcactggcactcttac900
cgttactgtttacccctgtgacaaaagcccggacaccagaaatgcctgttctggaaaacc960
gggctgctcagggcgatattactgcacccggcggtgctcgccgtttaacgggtgatcaga1020
ctgccgctctgcgtgattctcttagcgataaacctgcaaaaaatattattttgctgattg1080
gcgatgggatgggggactcggaaattactgccgcacgtaattatgccgaaggtgcgggcg1140
gcttttttaaaggtatagatgccttaccgcttaccgggcaatacactcactatgcgctga1200
ataaaaaaaccggcaaaccggactacgtcaccgactcggctgcatcagcaaccgcctggt1260
caaccggtgtcaaaacctataacggcgcgctgggcgtcgatattcacgaaaaagatcacc1320
caacgattctggaaatggcaaaagccgcaggtctggcgaccggtaacgtttctaccgcag1380
agttgcaggatgccacgcccgctgcgctggtggcacatgtgacctcgcgcaaatgctacg1440
gtccgagcgcgaccagtgaaaaatgtccgggtaacgctctggaaaaaggcggaaaaggat1500
cgattaccgaacagctgcttaacgctcgtgccgacgttacgcttggcggcggcgcaaaaa1560
cctttgctgaaacggcaaccgctggtgaatggcagggaaaaacgctgcgtgaacaggcac1620
aggcgcgtggttatcagttggtgagcgatgctgcctcactgaattcggtgacggaagcga1680
atcagcaaaaacccctgcttggcctgtttgctgacggcaatatgccagtgcgctggctag1740
gaccgaaagcaacgtaccatggcaatatcgataagcccgcagtcacctgtacgccaaatc1800
cgcaacgtaatgacagtgtaccaaccctggcgcagatgaccgacaaagccattgaattgt1860
tgagtaaaaatgagaaaggctttttcctgcaagttgaaggtgcgtcaatcgataaacagg1920
atcatgctgcgaatccttgtgggcaaattggcgagacggtcgatctcgatgaagccgtac1980
aacgggcgctggaattcgctaaaaaggagggtaacacgctggtcatagtcaccgctgatc2040
acgcccacgccagccagattgttgcgccggataccaaagctccgggcctcacccaggcgc2100
taaataccaaagatggcgcagtgatggtgatgagttacgggaactccgaagaggattcac2160
aagaacataccggcagtcagttgcgtattgcggcgtatggcccgcatgccgccaatgttg2220
ttggactgaccgaccagaccgatctcttctacaccatgaaagccgctctggggctgaaat2280
aattcgatatggccgctgctgtgatgatgatgatgatgatgatgatgatggcccatggta2340
tatctccttcttaaagttaaacaaaattatttctagaggggaattgttatccgctcacaa2400
ttcccctatagtgagtcgtattaatttcgcgggatcgagatctcgatcctctacgccgga2460
cgcatcgtggccggcatcaccggcgccacaggtgcggttgctggcgcctatatcgccgac2520
atcaccgatggggaagatcgggctcgccacttcgggctcatgagcgcttgtttcggcgtg2580
ggtatggtggcaggccccgtggccgggggactgttgggcgccatctccttgcatgcacca2640
ttccttgcggcggcggtgctcaacggcctcaacctactactgggctgcttcctaatgcag2700
gagtcgcataagggagagcgtcgagatcccggacaccatcgaatggcgcaaaacctttcg2760
cggtatggcatgatagcgcccggaagagagtcaattcagggtggtgaatgtgaaaccagt2820
aacgttatacgatgtcgcagagtatgccggtgtctcttatcagaccgtttcccgcgtggt2880
gaaccaggccagccacgtttctgcgaaaacgcgggaaaaagtggaagcggcgatggcgga2940
gctgaattacattcccaaccgcgtggcacaacaactggcgggcaaacagtcgttgctgat3000
tggcgttgccacctccagtctggccctgcacgcgccgtcgcaaattgtcgcggcgattaa3060
atctcgcgccgatcaactgggtgccagcgtggtggtgtcgatggtagaacgaagcggcgt3120
cgaagcctgtaaagcggcggtgcacaatcttctcgcgcaacgcgtcagtgggctgatcat3180
taactatccgctggatgaccaggatgccattgctgtggaagctgcctgcactaatgttcc3240
ggcgttatttcttgatgtctctgaccagacacccatcaacagtattattttctcccatga3300
agacggtacgcgactgggcgtggagcatctggtcgcattgggtcaccagcaaatcgcgct3360
gttagcgggcccattaagttctgtctcggcgcgtctgcgtctggctggctggcataaata3420
tctcactcgcaatcaaattcagccgatagcggaacgggaaggcgactggagtgccatgtc3480
cggttttcaacaaaccatgcaaatgctgaatgagggcatcgttcccactgcgatgctggt3540
tgccaacgatcagatggcgctgggcgcaatgcgcgccattaccgagtccgggctgcgcgt3600
tggtgcggatatctcggtagtgggata3627
<210>6
<211>135
<212>rna
<213>sgrna
<400>6
ggauccuaauacgacucacuauagguguccgggcuuuugucacguuuaagagcuaugcug60
gaaacagcauagcaaguuuaaauaaggcuaguccguuaucaacuugaaaaaguggcaccg120
agucggugcuuuuuu135
- 还没有人留言评论。精彩留言会获得点赞!