一种嗜热重组II型普鲁兰酶及其应用的制作方法
本发明涉及一种嗜热重组ii型普鲁兰酶及其应用,属于基因工程技术领域。
背景技术:
普鲁兰酶(ec3.2.1.41)是一种能够水解支链淀粉、普鲁兰糖、α-极限糊精和β-极限糊精中α-1,6糖苷键的淀粉脱支酶。根据水解方式和产物的特异性,普鲁兰酶可以分为i型普鲁兰酶和ii型普鲁兰酶。i型普鲁兰酶专一性地水解普鲁兰糖和淀粉中的α-1,6糖苷键,产生麦芽三糖和线性寡糖;ii型普鲁兰酶是双功能酶,不仅能够水解普鲁兰糖和支链淀粉中的α-1,6糖苷键,具备i型普鲁兰酶功能,而且能够通过随机内切的方式水解淀粉和相关寡糖中的α-1,4糖苷键,具备α-淀粉酶功能。普鲁兰酶在糖浆生产、柠檬酸发酵、工业酿造、制备抗性淀粉和分支环糊精方面具有重要应用。
工业中淀粉酶法加工一般分为两步,先是将α-淀粉酶与淀粉混合在95-105℃,ph6.0左右环境进行液化,之后加入糖化酶在60-65℃,ph4.0-4.5环境进行糖化反应。嗜热ii型普鲁兰酶天然具有优良的酶学性质,在淀粉的液化步骤中与α-淀粉酶混合使用不仅可以提高淀粉液化效率,而且可以减少接下来糖化反应的负担,明显缩短反应周期。
传统的淀粉酶法中液化和糖化步骤反应条件是不同的,步骤转换中反应参数的调节会对整个加工过程产生很多负面影响。比如总体反应时间过长;ph的变化会导致大量盐离子的产生;反应中经常产生一些多余的副产物,如潘糖,异潘糖,异麦芽糖等。
筛选新的具有高催化效率和耐热性的ii型普鲁兰酶可以显著提高淀粉酶解效率,降低糖浆生产成本。更重要的是,如果新的ii型普鲁兰酶在高温下具有良好的热稳定性,那么淀粉酶解就可以始终维持在高温下进行,这就可以显著提高糖浆产物浓度,降低染菌几率和总体操作时间。然而,目前报道的ii型普鲁兰酶普遍催化效率低,热稳定性差。如thermococcussiculihj21来源的ii型普鲁兰酶催化效率为11.3u/mg,thermococcushydrothermalis来源的ii型普鲁兰酶在95℃的半衰期仅为10min。因此,提供一种高酶活的嗜热重组ii型普鲁兰酶对于工业淀粉加工有重要的应用价值。
技术实现要素:
本发明的第一个目的是提供一种重组大肠杆菌,是(1)表达了seqidno.3所编码的ii型普鲁兰酶;或,(2)表达了seqidno.1所编码的ii型普鲁兰酶,且在含有强还原试剂的培养环境中蛋白分泌能力增强。
在本发明的一种实施方式中,所述强还原试剂包括fe2+、co2+、dtt和/或β-巯基乙醇。
在本发明的一种实施方式中,以pet系列载体为表达载体。
在本发明的一种实施方式中,编码(1)中所述ii型普鲁兰酶的核苷酸序列如seqidno.4所示。
在本发明的一种实施方式中,编码(2)中所述ii型普鲁兰酶的核苷酸序列如seqidno.2所示。
在本发明的一种实施方式中,以大肠杆菌bl21(de3)为宿主。
本发明的第二个目的是提供上述的重组大肠杆菌的构建方法,其特征在于,合成ii型普鲁兰酶的核苷酸序列,连接至表达载体pet-24a(+)上,得到重组质粒,将标签序列sumo连接到重组质粒上,替换重组质粒中的t7标签,转化至大肠杆菌。
本发明的第三个目的是提供一种生产ii型普鲁兰酶的方法,是应用了上述的重组大肠杆菌进行发酵。
在本发明的一种实施方式中,将重组大肠杆菌接种于lb培养基中,35-38℃培养10-14h,将培养好的菌液按1%-5%的接种量接种于lb培养基中,35-38℃振荡培养至od6000.4-0.6后,加入终浓度1-2mmol/l的诱导剂iptg,15-16℃,200-220rpm振荡培养15-20h。
本发明的第四个目的是提供上述的重组枯草芽孢杆菌在糖浆生产、柠檬酸发酵、工业酿造、制备抗性淀粉或制备分支环糊精中的应用。
本发明的有益效果:
本发明通过在大肠杆菌中异源表达ii型普鲁兰酶,获得一种嗜热重组ii型普鲁兰酶,其最适ph为6.6,在ph5.8-8.0有较好的ph耐受性,最适温度为95℃,在95℃保温10h,剩余酶活大于50%,能够在强还原条件下展现出较高的比酶活,fe2+、co2+、dtt、β-巯基乙醇使sumo-pulpy比酶活提高40%以上;其中dtt的加入更使sumo-pulpy比酶活提升237.2%。
本发明还提供了ii型普鲁兰酶sumo-pulpy的组合截断突变体△28n+△791c,该酶突变体△28n+△791c最适ph为6.4,在ph5.8~8.0之间有良好的ph耐受性,△28n+△791c最适温度为100℃,在100℃下保温2h剩余酶活大于60%。突变体△28n+△791c的比酶活为32.18±0.92u/mg,是重组ii型普鲁兰酶sumo-pulpy(5.37±0.20u/mg)的5.99倍,具有重要的工业应用价值和潜力。
附图说明
图1:不同蛋白融合标签对ii型普鲁兰酶pulpy表达的影响。
图2:在大肠杆菌中表达的重组ii型普鲁兰酶sumo-pulpy的sds-page分析。其中,1:低分子量蛋白质marker;2:bl21(de3)-pet-24a(+)-his+sumo-pulpy细胞破碎上清液;3:通过镍柱纯化的重组ii型普鲁兰酶sumo-pulpy。
图3:重组ii型普鲁兰酶sumo-pulpy在不同ph条件下的相对酶活。
图4:重组ii型普鲁兰酶sumo-pulpy的ph稳定性分析。
图5:重组ii型普鲁兰酶sumo-pulpy在不同温度条件下的相对酶活。
图6:重组ii型普鲁兰酶sumo-pulpy的热稳定性分析。
图7:重组ii型普鲁兰酶sumo-pulpy对普鲁兰糖的降解产物分析。
图8:重组ii型普鲁兰酶sumo-pulpy对马铃薯直链淀粉的降解产物分析。
图9:sumo-pulpy的截断突变体在95℃下和100℃保温2h后剩余比酶活分析。
图10:组合截断突变体△28n+△791c在不同ph条件下的相对酶活。
图11:组合截断突变体△28n+△791c的ph稳定性分析。
图12:组合截断突变体△28n+△791c在不同温度条件下的相对酶活。
图13:100℃条件下,组合截断突变体△28n+△791c的热稳定性分析。
具体实施方式
(一)菌株及载体
大肠杆菌表达载体pet-24a(+)及菌株escherichiacolibl21(de3)购自于novagen公司。
(二)酶类及其他生化试剂
限制性内切酶、t4dna连接酶、primestarmaxdna聚合酶购于宝日医生物技术(北京)有限公司。纯化及质粒提取试剂盒购于天根生化科技(北京)有限公司。普鲁兰糖(pullulan)购于山东福瑞达生物科技有限公司;马铃薯直链淀粉(amylosefrompotato)和小分子寡糖标准品购于sigma-aldrich;蛋白胨(tryptone)、酵母提取物(yeastextract)购于英国oxoid公司,其余试剂为国产分析纯。
(三)培养基
lb培养基(g/l):酵母粉5.0,蛋白胨10.0,nacl10.0,ph7.0。
平板筛选培养基(g/l):酵母粉5.0,蛋白胨10.0,nacl10.0,琼脂20.0,ph7.0。
以下实施例中未作具体说明的分子生物学实验方法,均参照《分子克隆实验指南》(第三版)j.萨姆布鲁克一书中所列的具体方法进行,或者按照试剂盒和产品说明书进行。
实施例1ii型普鲁兰酶基因的克隆及重组表达
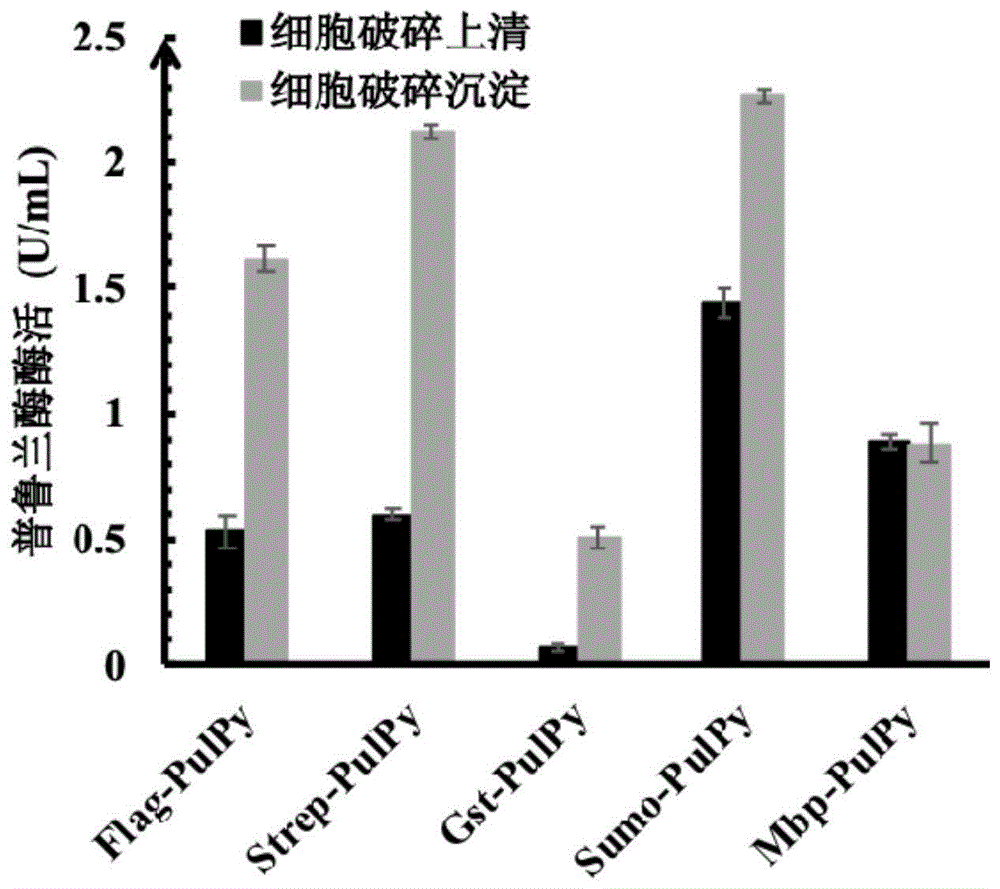
根据深海超嗜热嗜压古菌pyrococcusyayanosiich1来源的疑似ii型普鲁兰酶基因(thegenbankaccessionnumber:wp_013906427.1),对基因序列进行密码子序列,将优化后的基因序列(未经优化的基因序列在未连接蛋白标签的情况下,在大肠杆菌中几乎不表达。)seqidno.2交由通用生物系统(安徽)有限公司合成,连接至表达载体pet-24a(+)的bamhi,xhoi酶切位点之间,得到重组质粒pet-24a(+)-pulpy。接着,我们将标签序列flag,strep,gst,sumo,mbp交由通用生物系统(安徽)有限公司分别合成至pet-24a(+)-pulpy的ndei,bamhi酶切位点之间,对上述重组质粒的t7标签进行替换,并分别转化至大肠杆菌bl21(de3),比较重组ii型普鲁兰酶酶活。图1结果表明,添加flag,strep,gst,sumo,mbp标签时,重组ii型普鲁兰酶细胞内酶活分别为2.15,2.72,0.58,3.7,1.77u/ml,可见sumo标签对重组ii型普鲁兰酶表达效果较佳。接下来实验中,我们均以重组菌株bl21(de3)-pet-24a(+)-sumo-pulpy为研究对象。
为了获得重组ii型普鲁兰酶sumo-pulpy的纯蛋白,我们将一段同时包含his和sumo标签的核酸序列交由通用生物系统(安徽)有限公司合成至pet-24a(+)-pulpy的ndei,bamhi酶切位点之间,得到pet-24a(+)-his+sumo-pulpy,转化至大肠杆菌bl21(de3)。
将bl21(de3)-pet-24a(+)-his+sumo-pulpy接种于5mllb(50μg/ml的卡那霉素)培养液中,37℃培养过夜,将培养好的菌液按1%接种于50mllb(加有50μg/ml的卡那霉素),37℃振荡培养约2~3h(od600达到0.6)后加入终浓度2mmol/l的诱导剂iptg,16℃,220rpm振荡培养16h。12000rpm离心5min,收集培养基上清。dns法测定重组ii型普鲁兰酶sumo-pulpy的活力。sds-page结果(图2)表明,重组ii型普鲁兰酶sumo-pulpy在大肠杆菌中得到了表达,所表达的重组ii型普鲁兰酶sumo-pulpy经过镍柱亲和纯化之后,其蛋白质的含量达到总蛋白的90%以上。
实施例2重组ii型普鲁兰酶sumo-pulpy性质的测定
1.重组ii型普鲁兰酶sumo-pulpy的活性分析
重组ii型普鲁兰酶sumo-pulpy的活性测定采取3,5-二硝基水杨酸(dns)法,具体方法如下:100μl的反应体系(10μl终浓度100mm不同ph磷酸钾缓冲液、50μl终浓度3%普鲁兰多糖和40μl酶液)在一定温度下反应15min,加入100μldns反应液,沸水浴6min,流水速冷至室温,加蒸馏水稀释,混匀,测定od476。1个酶活力单位(u)定义为在测定条件下,每分钟释放相当于1μmol葡萄糖还原力的还原糖所需要的酶量。
2.重组ii型普鲁兰酶sumo-pulpy的最适ph和ph稳定性的测试
最适ph测定:将纯化后的sumo-pulpy在95℃下和100mmph5.8~8.0的磷酸钾缓冲液中进行酶促反应。
酶的ph稳定性测试:将酶液置于100mmph5.8~8.0的磷酸钾缓冲液中,在4℃下处理4h,然后在ph6.6及95℃下进行酶促反应,测定sumo-pulpy的剩余酶活。结果表明:sumo-pulpy的最适ph为6.6(图3);sumo-pulpy在ph5.8~8.0之间很稳定,除ph5.8处理4h后酶活力有约12%损失外,其余对此酶活力几乎没有影响(图4)。
3.重组ii型普鲁兰酶sumo-pulpy的最适温度及热稳定性测试
酶的最适温度的测定:在ph6.6的磷酸钾缓冲液中,于75~100℃下进行酶促反应。
酶的热稳定性测定:将同样酶量的酶液置于80℃、90℃、95℃和100℃中,分别处理2h、4h、6h、8h和10h,在ph6.6及95℃下进行酶促反应,测定sumo-pulpy的剩余酶活。酶反应最适温度测定结果(图5)表明,其最适温度为95℃。酶的热稳定性试验表明(图6),sumo-pulpy在95℃保温10h,剩余酶活大于50%,说明此酶热稳定性良好。
4.重组ii型普鲁兰酶sumo-pulpy的动力学参数的测定
以不同浓度的普鲁兰糖(1.25,2.5,5,10,20,40mg/ml)为底物,在最适条件下测定酶活性,计算相应的反应速度,利用米式方程双倒数法求得km值及vmax。结果表明:该酶的vmax为5.37±0.20u/mg,km为8.78±0.89mg/ml。
5.不同金属离子及化学试剂对重组ii型普鲁兰酶sumo-pulpy酶活的影响
在酶促反应体系中加入2mm的金属离子及一定浓度的化学试剂,研究其对sumo-pulpy活性的影响。当不添加金属离子及化学试剂时,sumo-pulpy在95℃,ph6.6条件下,比酶活为5.37±0.20u/mg,此时相对酶活为100%。结果(表1)表明:fe2+,co2+,dtt,β-巯基乙醇能够提高sumo-pulpy活力40%以上,其中dtt的加入使sumo-pulpy活力提升237.2%;k+,tritonx-100,tween-80对sumo-pulpy酶活有微弱的促进作用;其他试剂对sumo-pulpy活力有一定程度的抑制。
表1金属离子及化学试剂对sumo-pulpy活性的影响
6.重组ii型普鲁兰酶sumo-pulpy对普鲁兰糖和直链淀粉的降解产物分析
样品处理过程如下:使用适量纯酶液分别与1%普鲁兰糖,1%马铃薯直链淀粉混匀,95℃酶解6h,冷却至室温后12000r/min离心20min取上清,利用高效液相色谱(hplc,条件:hpersilnh2氨基色谱柱(4.6×250mm),柱温40℃,流动相(乙腈:水=67:33),流速1.0ml/min,进样量20μl)和maldi-tof/tof基质辅助激光解析电离串联飞行时间质谱仪分别对普鲁兰糖和马铃薯直链淀粉的酶解产物进行解析。
结果表明,普鲁兰糖水解产物中大多为麦芽三糖,且水解产物中没有潘糖和异潘糖出现,说明sumo-pulpy对普鲁兰糖的α-1,6糖苷键有专一性水解作用,属于普鲁兰酶(图7);sumo-pulpy对马铃薯直链淀粉的水解产物主要为五糖、六糖、七糖、八糖等低聚寡糖,说明该酶对马铃薯直链淀粉的α-1,4糖苷键也有一定水解能力,具有α-淀粉酶功能(图8)。综上所述,sumo-pulpy属于ii型普鲁兰酶。
实施例3ii型普鲁兰酶sumo-pulpy的截断突变体△28n+△791c的酶学性质分析
首先,分别将pulpyn端前28,33个氨基酸和c端第734,784,790,1021,1025,1068,1077位之后的氨基酸去掉,得到的9个pulpy截断体基因序列交由通用生物系统(安徽)有限公司分别合成至载体pet-24a(+)-his+sumo-pulpy的bamhi,xhoi酶切位点之间,将获得的9个新重组质粒分别转化至大肠杆菌bl21(de3)。结果表明,△735c在95℃下的比酶活是sumo-pulpy的0.33倍,100℃保温2h剩余比酶活为1.5u/mg,而△28n和△791c在95℃下的比酶活分别是sumo-pulpy的2.02和2.31倍,二者100℃保温2h剩余比酶活较sumo-pulpy也有一定程度提升(图9)。
之后将pulpyn端前28个氨基酸和c端第790位之后的氨基酸去掉,得到组合截断突变体△28n+△791c(氨基酸序列如seqidno.3所示)。△28n+△791c的表达纯化条件和酶学性质分析方法与sumo-pulpy相同。结果显示,△28n+△791c最适ph为6.4,较sumo-pulpy有明显向酸性偏移的趋势(图10);△28n+△791c在ph5.8~8.0之间有良好的ph耐受性(图11);△28n+△791c最适温度为100℃,较sumo-pulpy有5℃的提升(图12);△28n+△791c在100℃下的热稳定性较sumo-pulpy略有提升(图13)。动力学参数方面,△28n+△791c的vmax为32.18±0.92u/mg,比酶活是sumo-pulpy(5.37±0.20u/mg)的5.99倍;km为6.63±0.56mg/ml,较sumo-pulpy(8.78±0.89mg/ml)有所降低,表明△28n+△791c对底物的亲和能力有一定程度提升。
虽然本发明已以较佳实施例公开如上,但其并非用以限定本发明,任何熟悉此技术的人,在不脱离本发明的精神和范围内,都可做各种的改动与修饰,因此本发明的保护范围应该以权利要求书所界定的为准。
sequencelisting
<110>江南大学
<120>一种嗜热重组ii型普鲁兰酶及其应用
<160>4
<170>patentinversion3.3
<210>1
<211>1207
<212>prt
<213>人工合成
<400>1
metglyhishishishishishismetseraspsergluvalasngln
151015
glualalysprogluvallysprogluvallysprogluthrhisile
202530
asnleulysvalseraspglysersergluilephephelysilelys
354045
lysthrthrproleuargargleumetglualaphealalysarggln
505560
glylysglumetaspserleuargpheleutyraspglyileargile
65707580
glnalaaspglnthrprogluaspleuaspmetgluaspasnaspile
859095
ileglualahisarggluglnileglyglyglnargglyserargarg
100105110
valleuserleuphevalvalphevalvalleuglyserleuleuala
115120125
leuglnprogluvallysalaglygluprolysproleuasnvalile
130135140
ilevaltrphisglnhisglnprotyrtyrtyraspprovalglngly
145150155160
iletyrthrargprotrpvalargleuhisalaalaasnasntyrtrp
165170175
lysmetalatyrtyrleuserlystyrproaspvalhisalathrile
180185190
aspleuserglyserleuilealaglnleualaasptyrmetasngly
195200205
alalysaspiletyrglnileilethrglulysilealalysglyglu
210215220
proleuthrvalgluglulystrpleumetleuglnalaproglygly
225230235240
phepheasphisthrileprotrpasnglygluprovalthrasplys
245250255
asnglyasnproileargaspphetrpasnargtyrthrgluleulys
260265270
asnlysmetleuglnalalysalalystyralaasnleuproleuglu
275280285
gluglnlysvalalavalthrasngluphethrgluglnasptyrile
290295300
aspleualavalleupheasnleualatrpileasptyrasntyrile
305310315320
metasnthrprogluleulysalaleutyrglulysvalaspglugly
325330335
glytyrthrarggluaspvalargthrvalleulyshisglnmettrp
340345350
leuleuasnhisthrpheglugluhisglulysileasnleuleuleu
355360365
glyasnglyasnvalgluvalthrvalvalprotyralahisproile
370375380
glyproileleuasnasppheglytrpglugluasppheaspalahis
385390395400
vallyslysalahisgluleutyrlyslystyrleuglyalaglylys
405410415
valthrprolysglyglytrpalaalagluseralaleuasnasplys
420425430
thrleugluileleualagluasnglytrpglntrpvalmetthrasp
435440445
glnleuvalleuglnlysleuglyileprotyrthrvalgluasntyr
450455460
tyrlysprotrpvalalaglupheasnglyarglysiletyrleuphe
465470475480
proargasphisalaleuseraspargvalglyphethrtyrsergly
485490495
metasnglntyrglnalavalgluasppheileasngluleuleuarg
500505510
ileglnlysglnasntyraspglyserleuvaltyrvalilethrleu
515520525
aspglygluasnprotrpgluhistyrprotyraspglylysleuphe
530535540
leugluthrleutyrlysargleuthrgluleuglnargglnglyleu
545550555560
ileargthrleuthrproserglutyrilelysleutyrglyasplys
565570575
alaasnlysleuthrproglnmetmetgluargleuaspleuthrgly
580585590
aspasnvalglualaleuleulysalaglnserleuglygluleutyr
595600605
aspmetileglyvallysgluglumetglntrpproglusersertrp
610615620
ileaspglythrleuserthrtrpileglygluproglngluasntyr
625630635640
glytrptyrtrpleutyrleualaarglysalaleumetalaglnlys
645650655
asplysmetserglngluasntrpglulysalatyrglutyrleuleu
660665670
argalaglualaserasptrpphetrptrptyrglyseraspglnser
675680685
serglyglnasptyrthrpheaspargtyrphelysthrtyrleutyr
690695700
gluiletyrargleualaglyleugluproprosertyrleutyrgly
705710715720
asntyrpheproaspglygluprotyrthrileargalaleuglugly
725730735
leuglygluglyglnvallysglutyrsersermetserproleuala
740745750
gluglyvalservaltyrpheaspglygluglyvalhisphevalval
755760765
lysglyasnleuglulysphegluileseriletyrglulysglyglu
770775780
argvalglyasnthrphethrleuleuglngluargproglygluleu
785790795800
lystyrserleuphepropheserargaspservalglyleuleuile
805810815
thrlyshisvalvaltyrargaspglylysalagluiletyralaala
820825830
thrasptyrgluasnthrglulysvalglyglualaservallysgln
835840845
valaspglyglyvalgluilevalvalpropheasptyrilelysthr
850855860
progluaspphetyrphealavalserthrvallysaspglygluleu
865870875880
gluileilethrthrproilegluleulysleuprometgluvallys
885890895
glyvalproilevalaspvalvalaspprogluglyaspasptyrgly
900905910
proglythrtyrthrtyrprothraspprovalphevalprohishis
915920925
leuaspleuleuargpheargileleugluglnthraspalatyrval
930935940
metgluphetyrphelysgluleuglyglyasnvaltrpasnalapro
945950955960
asnglypheserleuglnileilegluvaltyrleuasppheargglu
965970975
glyglyasnthrseralailelysmetpheproaspglyproglyala
980985990
asnvalasnleuaspprogluhisprotrpaspleualaleuargile
99510001005
alaglytrpasptyrglyasnleuilevalleuproasnglythr
101010151020
valtyrglnglygluleuglnileseralaaspprovalasnasn
102510301035
lysileilevallysvalprolyslystyrileglnileaspglu
104010451050
asptyrglyleutrpglyvalvalleuvalglyserglnaspgly
105510601065
tyrglyproasplystrpargprovalalavalglualaglugln
107010751080
trpargleuglyglyalaaspglnglnalavalileaspasnleu
108510901095
alaproargvalvalaspleuleuvalprogluglyphelyspro
110011051110
thrglnglugluglnleusersertyraspleuglulyslysile
111511201125
leualathrvalleumetileproleuilegluglyserglygly
113011351140
glugluproalagluthrproarggluthralaileproalaglu
114511501155
serprothrthrthrglualaprothrgluthrglnserthrthr
116011651170
thrserglnglyprothrgluthrglnthrglyglyglyilecys
117511801185
glyprovalalaleuleuglyleuvalmetthrproleuleuleu
119011951200
argargargarg
1205
<210>2
<211>3624
<212>dna
<213>人工合成
<400>2
atgggtcaccaccaccaccaccacatgtcggactcagaagtcaatcaagaagctaagcca60
gaggtcaagccagaagtcaagcctgagactcacatcaatttaaaggtgtccgatggatct120
tcagagatcttcttcaagatcaaaaagaccactcctttaagaaggctgatggaagcgttc180
gctaaaagacagggtaaggaaatggactccttaagattcttgtacgacggtattagaatt240
caagctgatcagacccctgaagatttggacatggaggataacgatattattgaggctcac300
agagaacagattggtggccaacgcggatcccgtcgtgttctgagcctgtttgttgttttt360
gttgttctgggtagcctgctggcactgcagccggaagttaaagcaggtgaaccgaaaccg420
ctgaatgttattattgtttggcatcagcatcagccgtattattatgatccggttcagggt480
atttatacccgtccgtgggttcgtctgcatgcagcaaataattattggaaaatggcatat540
tatctgagcaaatatccggatgttcatgcaaccattgatctgagcggtagcctgattgca600
cagctggcagattatatgaatggtgcaaaagatatttatcagatcatcaccgaaaaaatc660
gcaaaaggtgaaccgctgaccgttgaagaaaaatggctgatgctgcaggcaccgggtggt720
ttttttgatcataccattccgtggaatggtgaaccggttaccgataaaaatggtaatccg780
attcgtgatttttggaatcgttataccgaactgaaaaataaaatgctgcaggcaaaagca840
aaatatgcaaatctgccgctggaagaacagaaagttgcagttaccaatgaatttaccgaa900
caggattatattgacctggcagttctgtttaatctggcatggattgattataattacatc960
atgaacaccccggaactgaaagcactgtatgaaaaagttgatgaaggtggttatacccgt1020
gaagatgttcgtaccgttctgaaacatcagatgtggctgctgaatcatacctttgaagaa1080
catgaaaaaatcaacctgctgctgggtaatggtaatgttgaagttaccgttgttccgtat1140
gcacatccgattggtccgattctgaatgattttggttgggaagaagattttgatgcacat1200
gttaaaaaagcacatgaactgtataaaaaatacctgggtgcaggtaaagttaccccgaaa1260
ggtggttgggcagcagaaagcgcactgaatgataaaaccctggaaattctggcagaaaat1320
ggttggcagtgggttatgaccgatcagctggttctgcagaaactgggtattccgtatacc1380
gttgaaaattattataaaccgtgggttgcagaatttaatggtcgtaaaatttacctgttc1440
ccgcgtgatcatgcactgagcgatcgtgttggttttacctatagcggtatgaatcagtat1500
caggcagttgaagattttattaatgagctgctgcgtattcagaaacagaattatgatggt1560
agcctggtttatgttattaccctggatggtgaaaatccgtgggaacattatccgtatgat1620
ggtaaactgtttctggaaaccctgtataaacgtctgaccgaactgcagcgtcagggtctg1680
attcgtaccctgaccccgagcgaatatattaaactgtatggtgataaagccaacaaactg1740
accccgcagatgatggaacgtctggatctgaccggtgataatgttgaagcactgctgaaa1800
gcacagagcctgggtgaactgtatgatatgattggtgttaaagaagaaatgcagtggccg1860
gaaagcagctggattgatggtacactgagcacctggattggtgaaccgcaggaaaattat1920
ggttggtattggctgtatctggcacgtaaagcactgatggcacagaaagataaaatgagc1980
caggaaaattgggaaaaagcatacgaatatctgctgcgtgcagaagcaagcgattggttt2040
tggtggtatggtagcgatcagagcagcggtcaggattatacctttgatcgttattttaaa2100
acctacctgtacgaaatttaccgtctggcaggtctggaaccgccgagctatctgtatggt2160
aattattttccggatggtgaaccgtataccattcgtgcactggaaggtctgggtgaaggt2220
caggttaaagaatatagcagcatgagcccgctggcagaaggtgttagcgtttattttgat2280
ggtgaaggtgttcattttgttgttaaaggtaatctggaaaaattcgaaatcagcatttac2340
gaaaaaggtgaacgtgttggtaatacctttaccctgctgcaggaacgtccgggtgaactg2400
aaatatagcctgtttccgtttagccgtgatagcgttggtctgctgattaccaaacatgtt2460
gtttatcgtgatggtaaagcagaaatttatgcagcaaccgattatgaaaataccgaaaaa2520
gttggtgaagcaagcgttaaacaggttgatggtggtgttgaaattgttgttccgtttgat2580
tatatcaaaaccccggaagatttttatttcgcagttagcaccgttaaagatggtgaactg2640
gaaattattaccaccccgattgaactgaaactgccgatggaagttaaaggtgttccgatt2700
gttgatgttgttgatccggaaggtgatgattatggtccgggtacatatacctatccgacc2760
gatccggtttttgttccgcatcatctggatctgctgcgttttcgtattctggaacagacc2820
gatgcatacgttatggaattttattttaaagagctgggtggtaatgtttggaatgcaccg2880
aatggttttagcctgcagattattgaagtttatctggattttcgtgagggtggtaatacc2940
agcgcaattaaaatgtttccggatggtccgggtgcaaatgttaatctggaccctgaacat3000
ccgtgggatctggcactgcgtattgcaggttgggattatggtaatctgattgttctgccg3060
aatggtacagtttatcagggtgaactgcagattagcgcagatccggttaataataaaatt3120
attgtgaaagtgcctaaaaaatacatccagattgatgaagattacggtctgtggggtgtt3180
gttctggttggtagccaggatggttatggtccggataaatggcgtccggttgcagttgaa3240
gcagaacagtggcgtctgggtggtgcagatcagcaggcagttattgataatctggcaccg3300
cgtgttgttgatctgctggttccggaaggttttaaaccgacccaggaagaacagctgagc3360
agctatgatctggaaaaaaaaattctggcaaccgttctgatgattccgctgattgaaggt3420
agcggtggtgaagaaccggcagaaaccccgcgtgaaaccgcaattccggcagaaagcccg3480
accaccaccgaagcaccgaccgaaacccagagcaccaccaccagccagggtccgaccgaa3540
acccagaccggtggtggtatttgtggtccggttgcactgctgggtctggttatgaccccg3600
ctgctgctgcgtcgtcgtcgttaa3624
<210>3
<211>872
<212>prt
<213>人工合成
<400>3
metglyhishishishishishismetseraspsergluvalasngln
151015
glualalysprogluvallysprogluvallysprogluthrhisile
202530
asnleulysvalseraspglysersergluilephephelysilelys
354045
lysthrthrproleuargargleumetglualaphealalysarggln
505560
glylysglumetaspserleuargpheleutyraspglyileargile
65707580
glnalaaspglnthrprogluaspleuaspmetgluaspasnaspile
859095
ileglualahisarggluglnileglyglyglnargglyserprolys
100105110
proleuasnvalileilevaltrphisglnhisglnprotyrtyrtyr
115120125
aspprovalglnglyiletyrthrargprotrpvalargleuhisala
130135140
alaasnasntyrtrplysmetalatyrtyrleuserlystyrproasp
145150155160
valhisalathrileaspleuserglyserleuilealaglnleuala
165170175
asptyrmetasnglyalalysaspiletyrglnileilethrglulys
180185190
ilealalysglygluproleuthrvalgluglulystrpleumetleu
195200205
glnalaproglyglyphepheasphisthrileprotrpasnglyglu
210215220
provalthrasplysasnglyasnproileargaspphetrpasnarg
225230235240
tyrthrgluleulysasnlysmetleuglnalalysalalystyrala
245250255
asnleuproleuglugluglnlysvalalavalthrasngluphethr
260265270
gluglnasptyrileaspleualavalleupheasnleualatrpile
275280285
asptyrasntyrilemetasnthrprogluleulysalaleutyrglu
290295300
lysvalaspgluglyglytyrthrarggluaspvalargthrvalleu
305310315320
lyshisglnmettrpleuleuasnhisthrpheglugluhisglulys
325330335
ileasnleuleuleuglyasnglyasnvalgluvalthrvalvalpro
340345350
tyralahisproileglyproileleuasnasppheglytrpgluglu
355360365
asppheaspalahisvallyslysalahisgluleutyrlyslystyr
370375380
leuglyalaglylysvalthrprolysglyglytrpalaalagluser
385390395400
alaleuasnasplysthrleugluileleualagluasnglytrpgln
405410415
trpvalmetthraspglnleuvalleuglnlysleuglyileprotyr
420425430
thrvalgluasntyrtyrlysprotrpvalalaglupheasnglyarg
435440445
lysiletyrleupheproargasphisalaleuseraspargvalgly
450455460
phethrtyrserglymetasnglntyrglnalavalgluasppheile
465470475480
asngluleuleuargileglnlysglnasntyraspglyserleuval
485490495
tyrvalilethrleuaspglygluasnprotrpgluhistyrprotyr
500505510
aspglylysleupheleugluthrleutyrlysargleuthrgluleu
515520525
glnargglnglyleuileargthrleuthrproserglutyrilelys
530535540
leutyrglyasplysalaasnlysleuthrproglnmetmetgluarg
545550555560
leuaspleuthrglyaspasnvalglualaleuleulysalaglnser
565570575
leuglygluleutyraspmetileglyvallysgluglumetglntrp
580585590
proglusersertrpileaspglythrleuserthrtrpileglyglu
595600605
proglngluasntyrglytrptyrtrpleutyrleualaarglysala
610615620
leumetalaglnlysasplysmetserglngluasntrpglulysala
625630635640
tyrglutyrleuleuargalaglualaserasptrpphetrptrptyr
645650655
glyseraspglnserserglyglnasptyrthrpheaspargtyrphe
660665670
lysthrtyrleutyrgluiletyrargleualaglyleuglupropro
675680685
sertyrleutyrglyasntyrpheproaspglygluprotyrthrile
690695700
argalaleugluglyleuglygluglyglnvallysglutyrserser
705710715720
metserproleualagluglyvalservaltyrpheaspglyglugly
725730735
valhisphevalvallysglyasnleuglulysphegluileserile
740745750
tyrglulysglygluargvalglyasnthrphethrleuleuglnglu
755760765
argproglygluleulystyrserleuphepropheserargaspser
770775780
valglyleuleuilethrlyshisvalvaltyrargaspglylysala
785790795800
gluiletyralaalathrasptyrgluasnthrglulysvalglyglu
805810815
alaservallysglnvalaspglyglyvalgluilevalvalprophe
820825830
asptyrilelysthrprogluaspphetyrphealavalserthrval
835840845
lysaspglygluleugluileilethrthrproilegluleulysleu
850855860
prometgluvallysglyvalpro
865870
<210>4
<211>2619
<212>dna
<213>人工合成
<400>4
atgggtcaccaccaccaccaccacatgtcggactcagaagtcaatcaagaagctaagcca60
gaggtcaagccagaagtcaagcctgagactcacatcaatttaaaggtgtccgatggatct120
tcagagatcttcttcaagatcaaaaagaccactcctttaagaaggctgatggaagcgttc180
gctaaaagacagggtaaggaaatggactccttaagattcttgtacgacggtattagaatt240
caagctgatcagacccctgaagatttggacatggaggataacgatattattgaggctcac300
agagaacagattggtggccaacgcggatccccgaaaccgctgaatgttattattgtttgg360
catcagcatcagccgtattattatgatccggttcagggtatttatacccgtccgtgggtt420
cgtctgcatgcagcaaataattattggaaaatggcatattatctgagcaaatatccggat480
gttcatgcaaccattgatctgagcggtagcctgattgcacagctggcagattatatgaat540
ggtgcaaaagatatttatcagatcatcaccgaaaaaatcgcaaaaggtgaaccgctgacc600
gttgaagaaaaatggctgatgctgcaggcaccgggtggtttttttgatcataccattccg660
tggaatggtgaaccggttaccgataaaaatggtaatccgattcgtgatttttggaatcgt720
tataccgaactgaaaaataaaatgctgcaggcaaaagcaaaatatgcaaatctgccgctg780
gaagaacagaaagttgcagttaccaatgaatttaccgaacaggattatattgacctggca840
gttctgtttaatctggcatggattgattataattacatcatgaacaccccggaactgaaa900
gcactgtatgaaaaagttgatgaaggtggttatacccgtgaagatgttcgtaccgttctg960
aaacatcagatgtggctgctgaatcatacctttgaagaacatgaaaaaatcaacctgctg1020
ctgggtaatggtaatgttgaagttaccgttgttccgtatgcacatccgattggtccgatt1080
ctgaatgattttggttgggaagaagattttgatgcacatgttaaaaaagcacatgaactg1140
tataaaaaatacctgggtgcaggtaaagttaccccgaaaggtggttgggcagcagaaagc1200
gcactgaatgataaaaccctggaaattctggcagaaaatggttggcagtgggttatgacc1260
gatcagctggttctgcagaaactgggtattccgtataccgttgaaaattattataaaccg1320
tgggttgcagaatttaatggtcgtaaaatttacctgttcccgcgtgatcatgcactgagc1380
gatcgtgttggttttacctatagcggtatgaatcagtatcaggcagttgaagattttatt1440
aatgagctgctgcgtattcagaaacagaattatgatggtagcctggtttatgttattacc1500
ctggatggtgaaaatccgtgggaacattatccgtatgatggtaaactgtttctggaaacc1560
ctgtataaacgtctgaccgaactgcagcgtcagggtctgattcgtaccctgaccccgagc1620
gaatatattaaactgtatggtgataaagccaacaaactgaccccgcagatgatggaacgt1680
ctggatctgaccggtgataatgttgaagcactgctgaaagcacagagcctgggtgaactg1740
tatgatatgattggtgttaaagaagaaatgcagtggccggaaagcagctggattgatggt1800
acactgagcacctggattggtgaaccgcaggaaaattatggttggtattggctgtatctg1860
gcacgtaaagcactgatggcacagaaagataaaatgagccaggaaaattgggaaaaagca1920
tacgaatatctgctgcgtgcagaagcaagcgattggttttggtggtatggtagcgatcag1980
agcagcggtcaggattatacctttgatcgttattttaaaacctacctgtacgaaatttac2040
cgtctggcaggtctggaaccgccgagctatctgtatggtaattattttccggatggtgaa2100
ccgtataccattcgtgcactggaaggtctgggtgaaggtcaggttaaagaatatagcagc2160
atgagcccgctggcagaaggtgttagcgtttattttgatggtgaaggtgttcattttgtt2220
gttaaaggtaatctggaaaaattcgaaatcagcatttacgaaaaaggtgaacgtgttggt2280
aatacctttaccctgctgcaggaacgtccgggtgaactgaaatatagcctgtttccgttt2340
agccgtgatagcgttggtctgctgattaccaaacatgttgtttatcgtgatggtaaagca2400
gaaatttatgcagcaaccgattatgaaaataccgaaaaagttggtgaagcaagcgttaaa2460
caggttgatggtggtgttgaaattgttgttccgtttgattatatcaaaaccccggaagat2520
ttttatttcgcagttagcaccgttaaagatggtgaactggaaattattaccaccccgatt2580
gaactgaaactgccgatggaagttaaaggtgttccgtaa2619
- 还没有人留言评论。精彩留言会获得点赞!